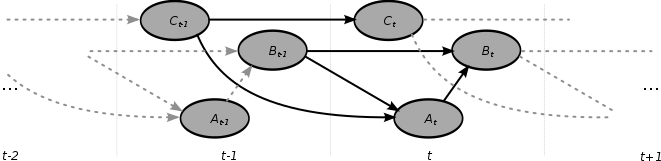
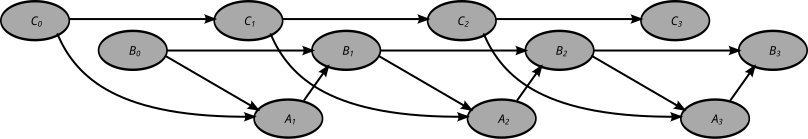
Una red bayesiana dinámica (DBN) es una red bayesiana (BN) que relaciona variables entre sí en pasos de tiempo adyacentes. Esto a menudo se denomina de dos timeslice BN (2TBN) porque se dice que en cualquier punto en el tiempo T, el valor de una variable se puede calcular a partir de los regresores internos y el valor inmediatamente anterior (tiempo T-1). Los DBN fueron desarrollados por Paul Dagum a principios de la década de 1990 en la Sección de Informática Médica de la Universidad de Stanford . [1] [2] Dagum desarrolló DBN para unificar y ampliar los modelos tradicionales de espacio de estado lineal , como los filtros de Kalman , modelos de predicción lineal y normal como ARMA.y modelos de dependencia simples como los modelos de Markov ocultos en una representación probabilística general y un mecanismo de inferencia para dominios arbitrarios no lineales y no normales dependientes del tiempo. [3] [4]
Hoy en día, los DBN son comunes en robótica y han mostrado potencial para una amplia gama de aplicaciones de minería de datos . Por ejemplo, se han utilizado en reconocimiento de voz , análisis forense digital , secuenciación de proteínas y bioinformática . DBN es una generalización de modelos ocultos de Markov y filtros de Kalman . [5]
Los DBN están relacionados conceptualmente con las redes booleanas probabilísticas [6] y, de manera similar, se pueden utilizar para modelar sistemas dinámicos en estado estable.
Ver también [ editar ]
Referencias [ editar ]
- ^ Paul Dagum ; Adam Galper ; Eric Horvitz (1992). "Modelos de redes dinámicas para la previsión" (PDF) . Actas de la Octava Conferencia sobre Incertidumbre en Inteligencia Artificial . Prensa AUAI: 41–48.
- ^ Paul Dagum ; Adam Galper ; Eric Horvitz ; Adam Seiver (1995). "Razonamiento incierto y pronóstico" . Revista Internacional de Pronósticos . 11 (1): 73–87. doi : 10.1016 / 0169-2070 (94) 02009-e .
- ^ Paul Dagum ; Adam Galper ; Eric Horvitz (junio de 1991). "Razonamiento probabilístico temporal: modelos de redes dinámicas para la previsión" (PDF) . Laboratorio de Sistemas de Conocimiento. Sección de Informática Médica, Universidad de Stanford .
- ^ Paul Dagum ; Adam Galper ; Eric Horvitz (1993). "Pronóstico de la apnea del sueño con modelos de red dinámica" . Actas de la Novena Conferencia sobre Incertidumbre en Inteligencia Artificial . Prensa AUAI: 64–71.
- ^ Stuart Russell ; Peter Norvig (2010). Inteligencia artificial: un enfoque moderno (PDF) (Tercera ed.). Prentice Hall . pag. 566. ISBN 978-0136042594. Archivado desde el original (PDF) el 20 de octubre de 2014 . Consultado el 22 de octubre de 2014 .
redes dinámicas bayesianas (que incluyen modelos ocultos de Markov y filtros de Kalman como casos especiales)
- ^ Harri Lähdesmäki ; Sampsa Hautaniemi ; Ilya Shmulevich ; Olli Yli-Harja (2006). "Relaciones entre redes probabilísticas booleanas y redes dinámicas bayesianas como modelos de redes reguladoras de genes" . Procesamiento de señales . 86 (4): 814–834. doi : 10.1016 / j.sigpro.2005.06.008 . PMC 1847796 . PMID 17415411 .
Lectura adicional [ editar ]
- Murphy, Kevin (2002). Redes dinámicas bayesianas: representación, inferencia y aprendizaje . UC Berkeley, División de Ciencias de la Computación.
- Ghahramani, Zoubin (1997). Aprendizaje de redes bayesianas dinámicas . Apuntes de conferencias en Ciencias de la Computación . 1387 . págs. 168-197. CiteSeerX 10.1.1.56.7874 . doi : 10.1007 / BFb0053999 . ISBN 978-3-540-64341-8.
- Friedman, N .; Murphy, K .; Russell, S. (1998). Aprendizaje de la estructura de redes probabilísticas dinámicas . UAI'98. Morgan Kaufmann. págs. 139-147. CiteSeerX 10.1.1.75.2969 .
Software [ editar ]
- bnt en GitHub : Bayes Net Toolbox para Matlab, por Kevin Murphy, (publicado bajo una licencia GPL )
- Conjunto de herramientas de modelos gráficos (GMTK): un conjunto de herramientas de código abierto y disponible públicamente para la creación rápida de prototipos de modelos estadísticos utilizando modelos gráficos dinámicos (DGM) y redes dinámicas bayesianas (DBN). GMTK se puede utilizar para aplicaciones e investigación en procesamiento del habla y el lenguaje, bioinformática, reconocimiento de actividades y cualquier aplicación de series de tiempo.
- DBmcmc : inferir redes bayesianas dinámicas con MCMC, para Matlab (software gratuito)
- Caja de herramientas GlobalMIT Matlab en Google Code : modelado de la red reguladora de genes a través de la optimización global de la red bayesiana dinámica (publicada bajo una licencia GPL )
- libDAI : biblioteca C ++ que proporciona implementaciones de varios métodos de inferencia (aproximados) para modelos gráficos discretos; admite gráficos de factores arbitrarios con variables discretas, incluidos los campos aleatorios de Markov discretos y las redes bayesianas (publicadas bajo la licencia FreeBSD )
- aGrUM : biblioteca C ++ (con enlaces de Python) para diferentes tipos de PGM, incluidas las redes bayesianas y las redes bayesianas dinámicas (publicadas bajo la GPLv3)
- FALCON : caja de herramientas de Matlab para contextualizar los modelos DBN de redes reguladoras con datos biológicos cuantitativos, incluidos varios esquemas de regularización para modelar el conocimiento biológico previo (publicado bajo la GPLv3)