Pirosecuenciación
La pirosecuenciación es un método de secuenciación de ADN (determinando el orden de los nucleótidos en el ADN) basado en el principio de "secuenciación por síntesis", en el que la secuenciación se realiza detectando el nucleótido incorporado por una ADN polimerasa . La pirosecuenciación se basa en la detección de luz basada en una reacción en cadena cuando se libera pirofosfato . De ahí el nombre pirosecuenciación.
El principio de pirosecuenciación fue descrito por primera vez en 1993 [1] por Bertil Pettersson , Mathias Uhlen y Pål Nyren mediante la combinación del método de secuenciación en fase sólida [2] utilizando perlas magnéticas recubiertas de estreptavidina con ADN polimerasa recombinante que carece de actividad exonucleasa 3 'a 5' (prueba -lectura) y detección de luminiscencia utilizando la enzima luciferasa de luciérnaga . [3] Una mezcla de tres enzimas ( ADN polimerasa , ATP sulfurilasa y luciferasa de luciérnaga ) y un nucleótido ( dNTP) se añaden al ADN monocatenario que se va a secuenciar y después de la incorporación de nucleótidos se mide la luz emitida. La intensidad de la luz determina si se han incorporado 0, 1 o más nucleótidos, mostrando así cuántos nucleótidos complementarios están presentes en la hebra molde. La mezcla de nucleótidos se elimina antes de agregar la siguiente mezcla de nucleótidos. Este proceso se repite con cada uno de los cuatro nucleótidos hasta que se determina la secuencia de ADN del molde monocatenario.
Un segundo método basado en solución para pirosecuenciación se describió en 1998 [4] por Mostafa Ronaghi , Mathias Uhlen y Pål Nyren . En este método alternativo, se introduce una enzima apirasa adicional para eliminar los nucleótidos que no son incorporados por la ADN polimerasa. Esto permitió que la mezcla de enzimas que incluye la ADN polimerasa , la luciferasa y la apirasa se agregaran al inicio y se mantuvieran durante todo el procedimiento, proporcionando así una configuración simple adecuada para la automatización. Un instrumento automatizado basado en este principio fue introducido al mercado al año siguiente por la empresa Pyrosequencing.
Una tercera variante de microfluidos del método de pirosecuenciación fue descrita en 2005 [5] por Jonathan Rothberg y colaboradores de la empresa 454 Life Sciences . Este enfoque alternativo para la pirosecuenciación se basó en el principio original de unir el ADN a secuenciar a un soporte sólido y mostraron que la secuenciación se podía realizar de una manera muy paralela utilizando un microarreglo microfabricado . Esto permitió la secuenciación de ADN de alto rendimiento y se introdujo en el mercado un instrumento automatizado. Este se convirtió en el primer instrumento de secuenciación de próxima generación que inició una nueva era en la investigación genómica , con una rápida caída de los precios de la secuenciación de ADN, lo que permitiósecuenciación del genoma completo a precios asequibles.
Procedimiento
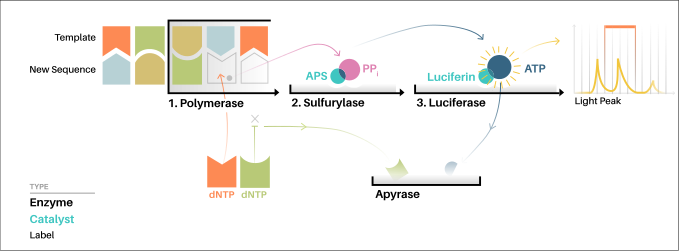
La "secuenciación por síntesis" implica tomar una sola hebra del ADN para secuenciar y luego sintetizar su hebra complementaria enzimáticamente. El método de pirosecuenciación se basa en detectar la actividad de la ADN polimerasa (una enzima sintetizadora de ADN) con otra enzima quimioluminiscente . Esencialmente, el método permite secuenciar una sola hebra de ADN sintetizando la hebra complementaria a lo largo de ella, un par de bases a la vez, y detectando qué base se agregó realmente en cada paso. La plantilla de ADN está inmóvil y las soluciones de nucleótidos A, C, G y Tse añaden secuencialmente y se retiran de la reacción. La luz se produce solo cuando la solución de nucleótidos complementa la primera base no apareada de la plantilla. La secuencia de soluciones que producen señales quimioluminiscentes permite la determinación de la secuencia de la plantilla. [6]
Para la versión basada en solución de Pyrosequencing, la plantilla de ADN monocatenario ( ssDNA ) se hibrida con un cebador de secuenciación y se incuba con las enzimas ADN polimerasa , ATP sulfurilasa , luciferasa y apirasa , y con los sustratos adenosina 5´ fosfosulfato (APS) y luciferina .
- La adición de uno de los cuatro desoxinucleótidos trifosfatos ( dNTP ) (dATPαS, que no es un sustrato para una luciferasa, se agrega en lugar de dATP para evitar ruido) inicia el segundo paso. La ADN polimerasa incorpora los dNTP complementarios correctos en la plantilla. Esta incorporación libera pirofosfato (PPi).
- La ATP sulfurilasa convierte PPi en ATP en presencia de adenosina 5´ fosfosulfato. Este ATP actúa como sustrato para la conversión mediada por luciferasa de luciferina en oxiluciferina que genera luz visible en cantidades que son proporcionales a la cantidad. La luz producida en la reacción catalizada por luciferasa es detectada por una cámara y analizada en un programa.
- Los nucleótidos no incorporados y el ATP son degradados por la apirasa y la reacción puede reiniciarse con otro nucleótido.
El proceso se puede representar mediante las siguientes ecuaciones:
- PPi + APS → ATP + Sulfato (catalizado por ATP-sulfurilasa);
- ATP + luciferina + O2 → AMP + PPi + oxiluciferina + CO2 + hv (catalizada por luciferasa);
dónde:
- PPi es pirofosfato
- APS es adenosina 5-fosfosulfato;
- ATP es trifosfato de adenosina;
- O2 es una molécula de oxígeno;
- AMP es monofosfato de adenosina;
- CO2 es dióxido de carbono;
- hv es ligero.
Limitaciones
Actualmente, una limitación del método es que las longitudes de las lecturas individuales de la secuencia de ADN están en la vecindad de 300-500 nucleótidos, más cortas que las de 800-1000 obtenibles con métodos de terminación de cadena (por ejemplo, secuenciación de Sanger). Esto puede dificultar el proceso de ensamblaje del genoma , particularmente para secuencias que contienen una gran cantidad de ADN repetitivo . La falta de actividad de corrección de pruebas limita la precisión de este método.
Comercialización
La empresa Pyrosequencing AB en Uppsala, Suecia, fue fundada con capital de riesgo proporcionado por HealthCap con el fin de comercializar maquinaria y reactivos para secuenciar tramos cortos de ADN utilizando la técnica de pirosecuenciación. Pyrosequencing AB comenzó a cotizar en la Bolsa de Valores de Estocolmo en 1999. En 2003 se le cambió el nombre a Biotage . La línea de negocio de pirosecuenciación fue adquirida por Qiagen en 2008. La tecnología de pirosecuenciación obtuvo una licencia adicional para 454 Life Sciences . 454 desarrolló una tecnología de pirosecuenciación basada en matrices que surgió como una plataforma para la secuenciación de ADN a gran escala , que incluyesecuenciación del genoma y metagenómica .
Roche anunció la interrupción de la plataforma de secuenciación 454 en 2013 cuando su tecnología dejó de ser competitiva. [7]
Referencias
- ^ Nyren, Petersson y Uhlen (1993) "Minisecuenciación de ADN en fase sólida mediante un ensayo de detección de pirofosfato inorgánico luminométrico enzimático" Analytical Biochemistry 208 (1), 171-175, https://doi.org/10.1006/abio.1993.1024
- ^ Uhlen (1989) "Separación magnética del ADN" Nature 340: 733-4, https://doi.org/10.1038/340733a0
- ^ Nyren y Lundin (1985) "Método enzimático para el control continuo de la síntesis de pirofosfato inorgánico" Analytiocal Biochemistry 151 (2): 504-509. https://doi.org/10.1016/0003-2697(85)90211-8
- ^ Ronaghi, Uhlén y Nyrén (1998) "Un método de secuenciación basado en pirofosfato en tiempo real" Ciencia. 281 (5375): 363. https://doi.org/10.1126/science.281.5375.363 .
- ^ Marguiles et al (2005) "Secuenciación del genoma en reactores de picolitros de alta densidad microfabricados" Nature 437, 376-380. https://doi.org/doi:10.1038/nature03959 ;
- ^ QIAGEN. "Descripción general de la plataforma y la tecnología de pirosecuenciación" . Consultado el 4 de agosto de 2017 .
- ^ Hollmer, Mark (17 de octubre de 2013). "Roche para cerrar 454 Life Sciences ya que reduce el enfoque de secuenciación de genes" . Fierce Biotech .
Otras lecturas
- Metzker M. (2005). "Tecnologías emergentes en secuenciación de ADN" . Investigación del genoma . 15 (12): 1767–76. doi : 10.1101 / gr.3770505 . PMID 16339375 .
- Biotecnología
- Métodos de secuenciación de ADN
- Industria de las ciencias de la vida
- Biología Molecular