ADN
| Parte de una serie sobre |
| Genética |
|---|
 |
El ácido desoxirribonucleico ( / d i ɒ k s ɪ ˌ r aɪ b oʊ nj U ˌ k l i ɪ k , - ˌ k l eɪ - / ( escuchar )![]() ; [1] ADN ) es una molécula compuesta de dos polinucleótidos cadenas que se enrollan entre sí para formar una doble hélice que lleva instrucciones genéticas para el desarrollo, funcionamiento, crecimiento yreproducción de todos los organismos conocidos y muchos virus . El ADN y el ácido ribonucleico (ARN) son ácidos nucleicos . Junto a las proteínas , los lípidos y los carbohidratos complejos ( polisacáridos ), los ácidos nucleicos son uno de los cuatro tipos principales de macromoléculas que son esenciales para todas las formas de vida conocidas .
; [1] ADN ) es una molécula compuesta de dos polinucleótidos cadenas que se enrollan entre sí para formar una doble hélice que lleva instrucciones genéticas para el desarrollo, funcionamiento, crecimiento yreproducción de todos los organismos conocidos y muchos virus . El ADN y el ácido ribonucleico (ARN) son ácidos nucleicos . Junto a las proteínas , los lípidos y los carbohidratos complejos ( polisacáridos ), los ácidos nucleicos son uno de los cuatro tipos principales de macromoléculas que son esenciales para todas las formas de vida conocidas .
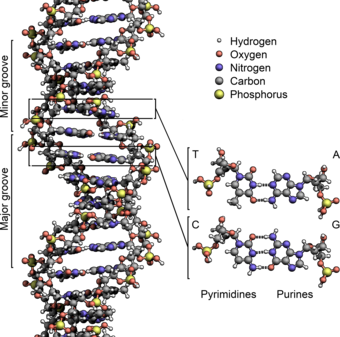
Las dos cadenas de ADN se conocen como polinucleótidos, ya que están compuestas por unidades monoméricas más simples llamadas nucleótidos . [2] [3] Cada nucleótido está compuesto por una de cuatro nucleobases que contienen nitrógeno ( citosina [C], guanina [G], adenina [A] o timina [T]), un azúcar llamado desoxirribosa y un grupo fosfato . Los nucleótidos están unidos entre sí en una cadena por enlaces covalentes.(conocido como enlace fosfo-diéster) entre el azúcar de un nucleótido y el fosfato del siguiente, lo que da como resultado una cadena principal alterna de azúcar-fosfato . Las bases nitrogenadas de las dos hebras de polinucleótidos separadas se unen entre sí, de acuerdo con las reglas de apareamiento de bases (A con T y C con G), con enlaces de hidrógeno para formar ADN de doble hebra. Las bases nitrogenadas complementarias se dividen en dos grupos, pirimidinas y purinas . En el ADN, las pirimidinas son timina y citosina; las purinas son adenina y guanina.
Ambas hebras de ADN de doble hebra almacenan la misma información biológica . Esta información se replica a medida que se separan las dos hebras. Una gran parte del ADN (más del 98% para los humanos) no es codificante , lo que significa que estas secciones no sirven como patrones para las secuencias de proteínas . Las dos hebras de ADN corren en direcciones opuestas entre sí y, por lo tanto, son antiparalelas . Unido a cada azúcar hay uno de los cuatro tipos de nucleobases (o bases ). Es la secuencia de estas cuatro nucleobases a lo largo de la columna vertebral la que codifica la información genética. Las cadenas de ARN se crean utilizando cadenas de ADN como plantilla en un proceso llamadotranscripción , donde las bases del ADN se intercambian por sus bases correspondientes excepto en el caso de la timina (T), para la cual el ARN sustituye al uracilo (U). [4] Según el código genético , estas cadenas de ARN especifican la secuencia de aminoácidos dentro de las proteínas en un proceso llamado traducción .
Dentro de las células eucariotas, el ADN está organizado en estructuras largas llamadas cromosomas . Antes de la división celular típica , estos cromosomas se duplican en el proceso de replicación del ADN , proporcionando un conjunto completo de cromosomas para cada célula hija. Los organismos eucariotas ( animales , plantas , hongos y protistas ) almacenan la mayor parte de su ADN dentro del núcleo celular como ADN nuclear y algunos en las mitocondrias como ADN mitocondrial o en cloroplastos como ADN de cloroplasto . [5]Por el contrario, los procariotas ( bacterias y arqueas ) almacenan su ADN solo en el citoplasma , en cromosomas circulares . Dentro de los cromosomas eucariotas, las proteínas de la cromatina , como las histonas , compactan y organizan el ADN. Estas estructuras de compactación guían las interacciones entre el ADN y otras proteínas, lo que ayuda a controlar qué partes del ADN se transcriben.
Propiedades
El ADN es un largo polímero hecha de unidades de repetición llamados nucleótidos , cada uno de los cuales por lo general se simboliza por una sola letra: o A , T , C , o G . [6] [7] La estructura del ADN es dinámica a lo largo de su longitud, siendo capaz de enrollarse en bucles estrechos y otras formas. [8] En todas las especies está compuesto por dos cadenas helicoidales, unidas entre sí por enlaces de hidrógeno . Ambas cadenas están enrolladas alrededor del mismo eje y tienen el mismo paso de 34 ångströms (3,4 nm ). El par de cadenas tiene un radio de 10 Å (1.0 nm). [9]Según otro estudio, cuando se midió en una solución diferente, la cadena de ADN midió 22-26 Å (2.2-2.6 nm) de ancho y una unidad de nucleótido midió 3.3 Å (0.33 nm) de largo. [10] Aunque cada nucleótido individual es muy pequeño, un polímero de ADN puede ser muy grande y contener cientos de millones de nucleótidos, como en el cromosoma 1 . El cromosoma 1 es el cromosoma humano más grande con aproximadamente 220 millones de pares de bases , y sería85 mm de largo si se endereza. [11]
El ADN no suele existir como una sola hebra, sino como un par de hebras que se mantienen juntas. [9] [12] Estos dos largos hilos se enrollan uno alrededor del otro, en forma de doble hélice . El nucleótido contiene tanto un segmento de la columna vertebral de la molécula (que mantiene unida a la cadena) como una nucleobase (que interactúa con la otra hebra de ADN en la hélice). Una nucleobase ligada a un azúcar se llama nucleósido , y una base ligada a un azúcar y a uno o más grupos fosfato se llama nucleótido . Un biopolímero que comprende múltiples nucleótidos enlazados (como en el ADN) se denomina polinucleótido .[13]
La columna vertebral de la cadena de ADN está formada por grupos alternos de fosfato y azúcar . [14] El azúcar en el ADN es 2-desoxirribosa , que es un azúcar pentosa (cinco carbonos ). Los azúcares están unidos por grupos fosfato que forman enlaces fosfodiéster entre el tercer y quinto átomos de carbono de los anillos de azúcar adyacentes. Estos se conocen como carbonos del extremo 3 ' (tres extremos principales) y del extremo 5' (cinco extremos principales), y el símbolo principal se utiliza para distinguir estos átomos de carbono de los de la base con la que la desoxirribosa forma un enlace glicosídico.. Por lo tanto, cualquier hebra de ADN normalmente tiene un extremo en el que hay un grupo fosfato unido al carbono 5 'de una ribosa (el 5' fosforilo) y otro extremo en el que hay un grupo hidroxilo libre unido al carbono 3 'de una ribosa. ribosa (el 3 'hidroxilo). La orientación de los carbonos 3 'y 5' a lo largo del esqueleto de azúcar-fosfato confiere direccionalidad (a veces llamada polaridad) a cada cadena de ADN. En una doble hélice de ácido nucleico , la dirección de los nucleótidos en una hebra es opuesta a su dirección en la otra hebra: las hebras son antiparalelas. Se dice que los extremos asimétricos de las cadenas de ADN tienen una direccionalidad de cinco extremos primarios (5 ′) y tres extremos primarios (3 ′), teniendo el extremo 5 ′ un grupo fosfato terminal y el extremo 3 ′ un grupo hidroxilo terminal. Una diferencia importante entre el ADN y el ARN es el azúcar, donde la 2-desoxirribosa en el ADN se reemplaza por la alternativa de azúcar pentosa ribosa en el ARN. [12]
La doble hélice del ADN se estabiliza principalmente por dos fuerzas: enlaces de hidrógeno entre nucleótidos e interacciones de apilamiento de bases entre nucleobases aromáticas . [16] Las cuatro bases que se encuentran en el ADN son adenina ( A ), citosina ( C ), guanina ( G ) y timina ( T ). Estas cuatro bases se unen al azúcar-fosfato para formar el nucleótido completo, como se muestra para el monofosfato de adenosina . Pares de adenina con timina y pares de guanina con citosina, formando AT y GC pares de bases . [17] [18]
Clasificación de nucleobase
Las nucleobases se clasifican en dos tipos: las purinas , A y G , que son compuestos heterocíclicos fusionados de cinco y seis miembros , y las pirimidinas , los anillos C y T de seis miembros . [12] Una quinta base nucleotídica de pirimidina, el uracilo ( U ), suele reemplazar a la timina en el ARN y se diferencia de la timina porque carece de un grupo metilo en su anillo. Además del ARN y el ADN, se han creado muchos análogos de ácidos nucleicos artificiales para estudiar las propiedades de los ácidos nucleicos o para su uso en biotecnología. [19]
Bases no canónicas
Las bases modificadas se encuentran en el ADN. La primera de ellas reconocida fue la 5-metilcitosina , que se encontró en el genoma de Mycobacterium tuberculosis en 1925. [20] La razón de la presencia de estas bases no canónicas en virus bacterianos ( bacteriófagos ) es evitar las enzimas de restricción presentes en las bacterias. Este sistema enzimático actúa, al menos en parte, como un sistema inmunológico molecular que protege a las bacterias de la infección por virus. [21] Las modificaciones de las bases citosina y adenina, las bases de ADN más comunes y modificadas, desempeñan funciones vitales en el control epigenético de la expresión génica en plantas y animales. [22]
Listado de bases no canónicas encontradas en el ADN
Se sabe que existen varias bases no canónicas en el ADN. [23] La mayoría de estos son modificaciones de las bases canónicas más uracilo.
- Adenosina modificada
- N6-carbamoil-metiladenina
- N6-metiadenina
- Guanina modificada
- 7-Deazaguanina
- 7-metilguanina
- Citosina modificada
- N4-metilcitosina
- 5-carboxilcitosina
- 5-formilcitosina
- 5-glicosilhidroximetilcitosina
- 5-hidroxicitosina
- 5-metilcitosina
- Timidina modificada
- α-glutamitimidina
- α-putresciniltilina
- Uracilo y modificaciones
- Base J
- Uracil
- 5-dihidroxipentauracilo
- 5-hidroximetildesoxiuracilo
- Otros
- Desoxiarqueosina
- 2,6-diaminopurina (2-aminoadenina)
Surcos
Las hebras helicoidales gemelas forman la columna vertebral del ADN. Se puede encontrar otra doble hélice trazando los espacios, o ranuras, entre las hebras. Estos huecos son adyacentes a los pares de bases y pueden proporcionar un sitio de unión . Como las hebras no están ubicadas simétricamente entre sí, las ranuras tienen un tamaño desigual. Un surco, el surco principal, tiene 22 ångströms (2,2 nm) de ancho y el otro, el surco menor, tiene 12 Å (1,2 nm) de ancho. [24] El ancho del surco mayor significa que los bordes de las bases son más accesibles en el surco mayor que en el menor. Como resultado, las proteínas, como los factores de transcripción, que pueden unirse a secuencias específicas en el ADN de doble hebra, suelen entrar en contacto con los lados de las bases expuestas en el surco principal. [25]Esta situación varía en conformaciones inusuales de ADN dentro de la célula (ver más abajo) , pero los surcos mayor y menor siempre se nombran para reflejar las diferencias de tamaño que se verían si el ADN se retorciera a la forma B ordinaria.
Emparejamiento de bases
En una doble hélice de ADN, cada tipo de nucleobase en una hebra se une con solo un tipo de nucleobase en la otra hebra. A esto se le llama emparejamiento de bases complementarias . Las purinas forman enlaces de hidrógeno a pirimidinas, con la adenina uniéndose solo a la timina en dos enlaces de hidrógeno y la citosina uniéndose solo a la guanina en tres enlaces de hidrógeno. Esta disposición de dos nucleótidos que se unen a través de la doble hélice (del anillo de seis carbonos al anillo de seis carbonos) se denomina par de bases de Watson-Crick. El ADN con alto contenido de GC es más estable que el ADN con bajo contenido de GC . Un par de bases de Hoogsteen (el hidrógeno que une el anillo de 6 carbonos al anillo de 5 carbonos) es una rara variación del emparejamiento de bases. [26] Como los enlaces de hidrógeno no soncovalentes , se pueden romper y volver a unir con relativa facilidad. Las dos hebras de ADN en una doble hélice se pueden separar como una cremallera, ya sea por una fuerza mecánica o por alta temperatura . [27] Como resultado de esta complementariedad de pares de bases, toda la información en la secuencia de doble hebra de una hélice de ADN se duplica en cada hebra, que es vital en la replicación del ADN. Esta interacción reversible y específica entre pares de bases complementarios es fundamental para todas las funciones del ADN en los organismos. [7]
ssDNA frente a dsDNA
Como se señaló anteriormente, la mayoría de las moléculas de ADN son en realidad dos hebras de polímero, unidas en forma helicoidal por enlaces no covalentes; esta estructura bicatenaria ( dsDNA ) se mantiene en gran parte por las interacciones de apilamiento de bases intracadena, que son más fuertes para las pilas G, C. Las dos hebras pueden separarse, un proceso conocido como fusión, para formar dos moléculas de ADN de una sola hebra ( ssDNA ). La fusión ocurre a alta temperatura, bajo contenido de sal y pH alto (el pH bajo también derrite el ADN, pero dado que el ADN es inestable debido a la depurinación ácida, rara vez se usa un pH bajo).
La estabilidad de la forma de dsDNA depende no solo del contenido de GC (% G, pares de bases C ) sino también de la secuencia (dado que el apilamiento es específico de la secuencia) y también de la longitud (las moléculas más largas son más estables). La estabilidad se puede medir de varias formas; una forma común es la "temperatura de fusión", que es la temperatura a la que el 50% de las moléculas bicatenarias se convierten en moléculas monocatenarias; la temperatura de fusión depende de la fuerza iónica y la concentración de ADN. Como resultado, es tanto el porcentaje de pares de bases de GC como la longitud total de una doble hélice de ADN lo que determina la fuerza de la asociación entre las dos cadenas de ADN. Hélices de ADN largas con un GC altoEl contenido tiene hebras de interacción más fuerte, mientras que las hélices cortas con alto contenido de AT tienen hebras de interacción más débil. [28] En biología, las partes de la doble hélice de ADN que necesitan separarse fácilmente, como la caja TATAAT Pribnow en algunos promotores , tienden a tener un alto contenido de AT , lo que hace que las hebras sean más fáciles de separar. [29]
En el laboratorio, la fuerza de esta interacción se puede medir encontrando la temperatura necesaria para romper la mitad de los enlaces de hidrógeno, su temperatura de fusión (también llamada valor T m ). Cuando todos los pares de bases en una doble hélice de ADN se funden, las hebras se separan y existen en solución como dos moléculas completamente independientes. Estas moléculas de ADN monocatenario no tienen una forma común única, pero algunas conformaciones son más estables que otras. [30]
Sentido y antisentido
Una secuencia de ADN se denomina secuencia "con sentido" si es la misma que la de una copia de ARN mensajero que se traduce en proteína. [31] La secuencia en la hebra opuesta se llama secuencia "antisentido". Tanto las secuencias sentido como las antisentido pueden existir en diferentes partes de la misma hebra de ADN (es decir, ambas hebras pueden contener secuencias tanto con sentido como antisentido). Tanto en procariotas como en eucariotas, se producen secuencias de ARN antisentido, pero las funciones de estos ARN no están del todo claras. [32] Una propuesta es que los ARN antisentido están involucrados en la regulación de la expresión génica a través del emparejamiento de bases ARN-ARN. [33]
Algunas secuencias de ADN en procariotas y eucariotas, y más en plásmidos y virus , difuminan la distinción entre cadenas con sentido y antisentido al tener genes superpuestos . [34] En estos casos, algunas secuencias de ADN cumplen una doble función: codifican una proteína cuando se leen a lo largo de una hebra y una segunda proteína cuando se leen en la dirección opuesta a lo largo de la otra hebra. En las bacterias , esta superposición puede estar involucrada en la regulación de la transcripción de genes, [35] mientras que en los virus, la superposición de genes aumenta la cantidad de información que puede codificarse dentro del pequeño genoma viral. [36]
Superenrollamiento
El ADN se puede retorcer como una cuerda en un proceso llamado superenrollamiento del ADN . Con el ADN en su estado "relajado", una hebra generalmente rodea el eje de la doble hélice una vez cada 10,4 pares de bases, pero si el ADN se retuerce, las hebras se vuelven más apretadas o más flojas. [37] Si el ADN se tuerce en la dirección de la hélice, se trata de un superenrollamiento positivo y las bases se mantienen más juntas. Si se tuercen en la dirección opuesta, se trata de un superenrollamiento negativo y las bases se separan más fácilmente. En la naturaleza, la mayor parte del ADN tiene un ligero superenrollamiento negativo que es introducido por enzimas llamadas topoisomerasas . [38]Estas enzimas también son necesarias para aliviar las tensiones de torsión introducidas en las hebras de ADN durante procesos como la transcripción y la replicación del ADN . [39]
Estructuras de ADN alternativas
El ADN existe en muchas conformaciones posibles que incluyen las formas A-ADN , B-ADN y Z-ADN , aunque solo se han observado directamente B-ADN y Z-ADN en organismos funcionales. [14] La conformación que adopta el ADN depende del nivel de hidratación, la secuencia del ADN, la cantidad y dirección del superenrollamiento, las modificaciones químicas de las bases, el tipo y concentración de iones metálicos y la presencia de poliaminas en solución. [40]
Los primeros informes publicados sobre patrones de difracción de rayos X de ADN-A —y también ADN-B— utilizaron análisis basados en transformaciones de Patterson que proporcionaron solo una cantidad limitada de información estructural para las fibras orientadas de ADN. [41] [42] Luego, Wilkins et al. Propusieron un análisis alternativo . , en 1953, para los patrones de difracción-dispersión de rayos X de ADN-B in vivo de fibras de ADN altamente hidratadas en términos de cuadrados de funciones de Bessel . [43] En la misma revista, James Watson y Francis Crick presentaron su modelado molecularanálisis de los patrones de difracción de rayos X del ADN para sugerir que la estructura era una doble hélice. [9]
Aunque la forma B-DNA es más común en las condiciones que se encuentran en las células, [44] no es una conformación bien definida, sino una familia de conformaciones de DNA relacionadas [45] que se producen a los altos niveles de hidratación presentes en las células. Sus correspondientes patrones de difracción y dispersión de rayos X son característicos de los paracristales moleculares con un grado significativo de desorden. [46] [47]
En comparación con B-DNA, la forma A-DNA es una espiral derecha más ancha , con un surco menor ancho y poco profundo y un surco mayor más estrecho y profundo. La forma A se presenta en condiciones no fisiológicas en muestras de ADN parcialmente deshidratadas, mientras que en la célula puede producirse en pares híbridos de cadenas de ADN y ARN y en complejos enzima-ADN. [48] [49] Los segmentos de ADN donde las bases han sido modificados químicamente por metilación pueden sufrir un cambio más grande en la conformación y adoptar la forma Z . Aquí, las hebras giran alrededor del eje helicoidal en una espiral hacia la izquierda, lo opuesto a la forma B más común. [50]Estas estructuras inusuales pueden ser reconocidas por proteínas de unión a ADN-Z específicas y pueden estar involucradas en la regulación de la transcripción. [51]
Química alternativa del ADN
Durante muchos años, los exobiólogos han propuesto la existencia de una biosfera en la sombra , una biosfera microbiana postulada de la Tierra que utiliza procesos bioquímicos y moleculares radicalmente diferentes a los de la vida actualmente conocida. Una de las propuestas fue la existencia de formas de vida que utilizan arsénico en lugar de fósforo en el ADN . Se anunció un informe en 2010 sobre la posibilidad de la bacteria GFAJ-1 , [52] [53] aunque la investigación fue cuestionada, [53] [54] y la evidencia sugiere que la bacteria previene activamente la incorporación de arsénico en la columna vertebral del ADN. y otras biomoléculas. [55]
Estructuras cuádruplex
En los extremos de los cromosomas lineales hay regiones especializadas de ADN llamadas telómeros . La función principal de estas regiones es permitir que la célula replique los extremos de los cromosomas utilizando la enzima telomerasa , ya que las enzimas que normalmente replican el ADN no pueden copiar los extremos 3 ′ de los cromosomas. [56] Estos casquetes cromosómicos especializados también ayudan a proteger los extremos del ADN y evitan que los sistemas de reparación del ADN en la célula los traten como daños a corregir. [57] En las células humanas , los telómeros suelen ser longitudes de ADN monocatenario que contienen varios miles de repeticiones de una secuencia TTAGGG simple. [58]
Estas secuencias ricas en guanina pueden estabilizar los extremos de los cromosomas formando estructuras de conjuntos apilados de unidades de cuatro bases, en lugar de los pares de bases habituales que se encuentran en otras moléculas de ADN. Aquí, cuatro bases de guanina, conocidas como tétrada de guanina , forman una placa plana. Estas unidades planas de cuatro bases se apilan una encima de la otra para formar una estructura G-quadruplex estable . [60] Estas estructuras se estabilizan mediante enlaces de hidrógeno entre los bordes de las bases y la quelación de un ión metálico en el centro de cada unidad de cuatro bases. [61] También se pueden formar otras estructuras, con el conjunto central de cuatro bases provenientes de una sola hebra doblada alrededor de las bases, o de varias hebras paralelas diferentes, cada una aportando una base a la estructura central.
Además de estas estructuras apiladas, los telómeros también forman grandes estructuras de bucle llamadas bucles de telómeros o bucles en T. Aquí, el ADN monocatenario se enrolla en un círculo largo estabilizado por proteínas de unión a telómeros. [62] Al final del bucle T, el ADN del telómero monocatenario se mantiene en una región del ADN bicatenario mediante la cadena del telómero que interrumpe el ADN de doble hélice y el apareamiento de bases con una de las dos cadenas. Esto de triple cadena estructura se denomina un bucle de desplazamiento o D-loop . [60]
| Rama única | Varias ramas |
ADN ramificado
En el ADN, el deshilachado ocurre cuando existen regiones no complementarias al final de una doble hebra de ADN que de otro modo sería complementaria. Sin embargo, puede producirse ADN ramificado si se introduce una tercera hebra de ADN y contiene regiones contiguas capaces de hibridar con las regiones deshilachadas de la doble hebra preexistente. Aunque el ejemplo más simple de ADN ramificado involucra solo tres cadenas de ADN, también son posibles complejos que involucran cadenas adicionales y múltiples ramas. [63] El ADN ramificado se puede utilizar en nanotecnología para construir formas geométricas; consulte la sección sobre usos en tecnología a continuación.
Bases artificiales
Se han sintetizado varias nucleobases artificiales y se han incorporado con éxito en el análogo de ADN de ocho bases llamado ADN de Hachimoji . Denominadas S, B, P y Z, estas bases artificiales son capaces de unirse entre sí de forma predecible (S – B y P – Z), mantener la estructura de doble hélice del ADN y transcribirse a ARN. Su existencia podría verse como una indicación de que no hay nada especial en las cuatro nucleobases naturales que evolucionaron en la Tierra. [64] [65] Por otro lado, el ADN está estrechamente relacionado con el ARNque no solo actúa como una transcripción del ADN sino que también realiza como máquinas moleculares muchas tareas en las células. Para ello, tiene que plegarse formando una estructura. Se ha demostrado que para permitir la creación de todas las estructuras posibles se requieren al menos cuatro bases para el ARN correspondiente , [66] mientras que también es posible un número mayor, pero esto iría en contra del Principio natural del menor esfuerzo .
Modificaciones químicas y empaquetamiento de ADN alterado
| citosina | 5-metilcitosina | timina |
Modificaciones de base y empaquetado de ADN
La expresión de los genes está influenciada por cómo se empaqueta el ADN en los cromosomas, en una estructura llamada cromatina . Las modificaciones de las bases pueden estar implicadas en el empaquetamiento, con regiones que tienen una expresión génica baja o nula que normalmente contienen altos niveles de metilación de bases de citosina . El empaquetamiento del ADN y su influencia en la expresión génica también puede ocurrir por modificaciones covalentes del núcleo de la proteína histona alrededor del cual el ADN está envuelto en la estructura de la cromatina o también por remodelación llevada a cabo por complejos de remodelación de cromatina (ver Remodelación de cromatina ). Además, existe una diafonía entre la metilación del ADN y la modificación de histonas, por lo que pueden afectar de manera coordinada la cromatina y la expresión génica.[67]
Por ejemplo, la metilación de citosina produce 5-metilcitosina , que es importante para la inactivación X de los cromosomas. [68] El nivel promedio de metilación varía entre organismos: el gusano Caenorhabditis elegans carece de metilación de citosina, mientras que los vertebrados tienen niveles más altos, con hasta un 1% de su ADN que contiene 5-metilcitosina. [69] A pesar de la importancia de la 5-metilcitosina, puede desaminarse para dejar una base de timina, por lo que las citosinas metiladas son particularmente propensas a mutaciones . [70] Otras modificaciones de bases incluyen la metilación de adenina en bacterias, la presencia de 5-hidroximetilcitosinaen el cerebro , [71] y la glicosilación del uracilo para producir la "base J" en los cinetoplastidos . [72] [73]
Daño
El ADN puede resultar dañado por muchos tipos de mutágenos , que cambian la secuencia del ADN . Los mutágenos incluyen agentes oxidantes , agentes de alquilación y también de alta energía de radiación electromagnética , tales como ultravioleta luz y los rayos X . El tipo de daño del ADN producido depende del tipo de mutágeno. Por ejemplo, la luz ultravioleta puede dañar el ADN al producir dímeros de timina , que son enlaces cruzados entre las bases de pirimidina. [75] Por otro lado, oxidantes como los radicales libres o el peróxido de hidrógenoproducen múltiples formas de daño, incluidas modificaciones de bases, particularmente de guanosina, y roturas de doble hebra. [76] Una célula humana típica contiene alrededor de 150.000 bases que han sufrido daño oxidativo. [77] De estas lesiones oxidativas, las más peligrosas son las roturas de doble hebra, ya que son difíciles de reparar y pueden producir mutaciones puntuales , inserciones , deleciones de la secuencia de ADN y translocaciones cromosómicas . [78] Estas mutaciones pueden causar cáncer . Debido a los límites inherentes a los mecanismos de reparación del ADN, si los humanos vivieran lo suficiente, eventualmente todos desarrollarían cáncer. [79] [80]Los daños al ADN que ocurren naturalmente , debido a procesos celulares normales que producen especies reactivas de oxígeno, las actividades hidrolíticas del agua celular, etc., también ocurren con frecuencia. Aunque la mayoría de estos daños se reparan, en cualquier célula puede quedar algo de daño en el ADN a pesar de la acción de los procesos de reparación. Estos daños restantes del ADN se acumulan con la edad en los tejidos postmitóticos de los mamíferos. Esta acumulación parece ser una importante causa subyacente del envejecimiento. [81] [82] [83]
Muchos mutágenos encajan en el espacio entre dos pares de bases adyacentes, esto se llama intercalación . La mayoría de los intercaladores son moléculas aromáticas y planas; los ejemplos incluyen bromuro de etidio , acridinas , daunomicina y doxorrubicina . Para que un intercalador se ajuste entre pares de bases, las bases deben separarse, distorsionando las hebras de ADN al desenrollar la doble hélice. Esto inhibe tanto la transcripción como la replicación del ADN, provocando toxicidad y mutaciones. [84] Como resultado, los intercaladores de ADN pueden ser carcinógenos y, en el caso de la talidomida, un teratógeno . [85] Otros como el benzo [a ] pireno diol epóxido y aflatoxina forman aductos de ADN que inducen errores en la replicación. [86] No obstante, debido a su capacidad para inhibir la transcripción y replicación del ADN, también se utilizan otras toxinas similares en la quimioterapia para inhibir las células cancerosas de crecimiento rápido. [87]
Funciones biologicas
El ADN generalmente se presenta como cromosomas lineales en eucariotas y cromosomas circulares en procariotas . El conjunto de cromosomas de una célula constituye su genoma ; el genoma humano tiene aproximadamente 3 mil millones de pares de bases de ADN organizados en 46 cromosomas. [88] La información transportada por el ADN se mantiene en la secuencia de fragmentos de ADN llamados genes . Transmisiónde la información genética en los genes se logra mediante el apareamiento de bases complementarias. Por ejemplo, en la transcripción, cuando una célula usa la información de un gen, la secuencia de ADN se copia en una secuencia de ARN complementaria mediante la atracción entre el ADN y los nucleótidos de ARN correctos. Por lo general, esta copia de ARN se usa para hacer una secuencia de proteína coincidente en un proceso llamado traducción , que depende de la misma interacción entre los nucleótidos de ARN. De manera alternativa, una célula puede simplemente copiar su información genética en un proceso llamado replicación del ADN . Los detalles de estas funciones se tratan en otros artículos; aquí la atención se centra en las interacciones entre el ADN y otras moléculas que median la función del genoma.
Genes y genomas
El ADN genómico se empaqueta de manera apretada y ordenada en el proceso llamado condensación de ADN , para adaptarse a los pequeños volúmenes disponibles de la célula. En eucariotas, el ADN se encuentra en el núcleo celular , con pequeñas cantidades en mitocondrias y cloroplastos . En los procariotas, el ADN se mantiene dentro de un cuerpo de forma irregular en el citoplasma llamado nucleoide . [89] La información genética de un genoma se encuentra dentro de los genes, y el conjunto completo de esta información en un organismo se denomina genotipo . Un gen es una unidad hereditaria y es una región del ADN que influye en una característica particular de un organismo. Los genes contienen unmarco de lectura abierto que se puede transcribir, y secuencias reguladoras tales como promotores y potenciadores , que controlan la transcripción del marco de lectura abierto.
En muchas especies , solo una pequeña fracción de la secuencia total del genoma codifica proteínas. Por ejemplo, solo alrededor del 1,5% del genoma humano consiste en exones que codifican proteínas , y más del 50% del ADN humano consiste en secuencias repetitivas no codificantes . [90] Las razones de la presencia de tanto ADN no codificante en los genomas eucariotas y las extraordinarias diferencias en el tamaño del genoma , o valor C , entre especies, representan un enigma de larga data conocido como el " enigma del valor C ". [91] Sin embargo, algunas secuencias de ADN que no codifican proteínas aún pueden codificar ARN funcional no codificante.moléculas, que participan en la regulación de la expresión génica . [92]
Algunas secuencias de ADN no codificantes desempeñan funciones estructurales en los cromosomas. Los telómeros y centrómeros suelen contener pocos genes, pero son importantes para la función y estabilidad de los cromosomas. [57] [94] Una forma abundante de ADN no codificante en humanos son los pseudogenes , que son copias de genes que han sido desactivados por mutación. [95] Estas secuencias suelen ser sólo fósiles moleculares , aunque ocasionalmente pueden servir como material genético en bruto para la creación de nuevos genes a través del proceso de duplicación y divergencia de genes . [96]
Transcripción y traducción
Un gen es una secuencia de ADN que contiene información genética y puede influir en el fenotipo de un organismo. Dentro de un gen, la secuencia de bases a lo largo de una hebra de ADN define una secuencia de ARN mensajero , que luego define una o más secuencias de proteínas. La relación entre las secuencias de nucleótidos de los genes y las secuencias de aminoácidos de las proteínas está determinada por las reglas de traducción , conocidas colectivamente como código genético . El código genético consta de "palabras" de tres letras llamadas codones formados a partir de una secuencia de tres nucleótidos (por ejemplo, ACT, CAG, TTT).
En la transcripción, los codones de un gen se copian en el ARN mensajero por la ARN polimerasa . Esta copia de ARN es luego decodificada por un ribosoma que lee la secuencia de ARN emparejando las bases del ARN mensajero para transferir ARN , que transporta aminoácidos. Dado que hay 4 bases en combinaciones de 3 letras, hay 64 codones posibles (4 3 combinaciones). Estos codifican los veinte aminoácidos estándar , dando a la mayoría de los aminoácidos más de un codón posible. También hay tres codones "de parada" o "sin sentido" que significan el final de la región codificante; estos son los codones TAG, TAA y TGA (UAG, UAA y UGA en el ARNm).
Replication
La división celular es esencial para que un organismo crezca, pero cuando una célula se divide, debe replicar el ADN en su genoma para que las dos células hijas tengan la misma información genética que su progenitor. La estructura bicatenaria del ADN proporciona un mecanismo simple para la replicación del ADN . Aquí, las dos hebras se separan y luego la secuencia de ADN complementaria de cada hebra es recreada por una enzima llamada ADN polimerasa . Esta enzima produce la hebra complementaria al encontrar la base correcta a través del emparejamiento de bases complementarias y unirla a la hebra original. Como las ADN polimerasas solo pueden extender una hebra de ADN en una dirección de 5 'a 3', se utilizan diferentes mecanismos para copiar las hebras antiparalelas de la doble hélice.[97] De esta manera, la base de la cadena antigua dicta qué base aparece en la nueva cadena, y la célula termina con una copia perfecta de su ADN.
Ácidos nucleicos extracelulares
Naked extracellular DNA (eDNA), most of it released by cell death, is nearly ubiquitous in the environment. Its concentration in soil may be as high as 2 μg/L, and its concentration in natural aquatic environments may be as high at 88 μg/L.[98] Various possible functions have been proposed for eDNA: it may be involved in horizontal gene transfer;[99] it may provide nutrients;[100] and it may act as a buffer to recruit or titrate ions or antibiotics.[101] Extracellular DNA acts as a functional extracellular matrix component in the biofilms of several bacterial species. It may act as a recognition factor to regulate the attachment and dispersal of specific cell types in the biofilm;[102] puede contribuir a la formación de biopelículas; [103] y puede contribuir a la fuerza física y resistencia de la biopelícula al estrés biológico. [104]
El ADN fetal libre de células se encuentra en la sangre de la madre y se puede secuenciar para determinar una gran cantidad de información sobre el feto en desarrollo. [105]
Bajo el nombre de ADN ambiental, el ADN electrónico se ha visto cada vez más utilizado en las ciencias naturales como una herramienta de estudio para la ecología , monitoreando los movimientos y la presencia de especies en el agua, el aire o la tierra, y evaluando la biodiversidad de un área. [106] [107]
Trampas extracelulares de neutrófilos
Las trampas extracelulares de neutrófilos (NET) son redes de fibras extracelulares, principalmente compuestas de ADN, que permiten que los neutrófilos , un tipo de glóbulo blanco, maten los patógenos extracelulares al tiempo que minimizan el daño a las células huésped.
Interacciones con proteínas
Todas las funciones del ADN dependen de las interacciones con las proteínas. Estas interacciones de proteínas pueden ser inespecíficas o la proteína puede unirse específicamente a una única secuencia de ADN. Las enzimas también pueden unirse al ADN y, de estos, las polimerasas que copian la secuencia de bases del ADN en la transcripción y replicación del ADN son particularmente importantes.
Proteínas de unión al ADN
Las proteínas estructurales que se unen al ADN son ejemplos bien conocidos de interacciones ADN-proteína no específicas. Dentro de los cromosomas, el ADN se mantiene en complejos con proteínas estructurales. Estas proteínas organizan el ADN en una estructura compacta llamada cromatina . En eucariotas, esta estructura implica la unión del ADN a un complejo de pequeñas proteínas básicas llamadas histonas , mientras que en los procariotas participan múltiples tipos de proteínas. [108] [109] Las histonas forman un complejo en forma de disco llamado nucleosoma , que contiene dos vueltas completas de ADN bicatenario envuelto alrededor de su superficie. Estas interacciones no específicas se forman a través de residuos básicos en las histonas, creando enlaces iónicos.al esqueleto ácido de azúcar-fosfato del ADN y, por lo tanto, son en gran medida independientes de la secuencia de bases. [110] Las modificaciones químicas de estos residuos de aminoácidos básicos incluyen metilación , fosforilación y acetilación . [111] Estos cambios químicos alteran la fuerza de la interacción entre el ADN y las histonas, haciendo que el ADN sea más o menos accesible a los factores de transcripción y cambiando la tasa de transcripción. [112] Otras proteínas de unión al ADN no específicas en la cromatina incluyen las proteínas del grupo de alta movilidad, que se unen al ADN doblado o distorsionado. [113] These proteins are important in bending arrays of nucleosomes and arranging them into the larger structures that make up chromosomes.[114]
A distinct group of DNA-binding proteins is the DNA-binding proteins that specifically bind single-stranded DNA. In humans, replication protein A is the best-understood member of this family and is used in processes where the double helix is separated, including DNA replication, recombination, and DNA repair.[115] These binding proteins seem to stabilize single-stranded DNA and protect it from forming stem-loops or being degraded by nucleases.
Por el contrario, otras proteínas han evolucionado para unirse a secuencias de ADN particulares. El más estudiado de estos son los diversos factores de transcripción , que son proteínas que regulan la transcripción. Cada factor de transcripción se une a un conjunto particular de secuencias de ADN y activa o inhibe la transcripción de genes que tienen estas secuencias cercanas a sus promotores. Los factores de transcripción hacen esto de dos formas. En primer lugar, pueden unirse a la ARN polimerasa responsable de la transcripción, ya sea directamente o mediante otras proteínas mediadoras; esto ubica la polimerasa en el promotor y le permite comenzar la transcripción. [117] Alternativamente, los factores de transcripción pueden unirse a enzimasque modifican las histonas en el promotor. Esto cambia la accesibilidad de la plantilla de ADN a la polimerasa. [118]
As these DNA targets can occur throughout an organism's genome, changes in the activity of one type of transcription factor can affect thousands of genes.[119] Consequently, these proteins are often the targets of the signal transduction processes that control responses to environmental changes or cellular differentiation and development. The specificity of these transcription factors' interactions with DNA come from the proteins making multiple contacts to the edges of the DNA bases, allowing them to "read" the DNA sequence. Most of these base-interactions are made in the major groove, where the bases are most accessible.[25]
Enzimas modificadoras de ADN
Nucleasas y ligasas
Las nucleasas son enzimas que cortan las cadenas de ADN catalizando la hidrólisis de los enlaces fosfodiéster . Las nucleasas que hidrolizan los nucleótidos de los extremos de las cadenas de ADN se denominan exonucleasas , mientras que las endonucleasas cortan dentro de las cadenas. Las nucleasas más utilizadas en biología molecular son las endonucleasas de restricción , que cortan el ADN en secuencias específicas. Por ejemplo, la enzima EcoRV que se muestra a la izquierda reconoce la secuencia de 6 bases 5′-GATATC-3 ′ y hace un corte en la línea horizontal. En la naturaleza, estas enzimas protegen a las bacterias contra los fagos.infección al digerir el ADN del fago cuando ingresa a la célula bacteriana, actuando como parte del sistema de modificación de restricción . [121] En tecnología, estas nucleasas específicas de secuencia se utilizan en la clonación molecular y la toma de huellas dactilares de ADN .
Las enzimas llamadas ADN ligasas pueden volver a unirse a las hebras de ADN cortadas o rotas. [122] Las ligasas son particularmente importantes en la replicación del ADN de la hebra rezagada , ya que unen los segmentos cortos de ADN producidos en la bifurcación de replicación en una copia completa de la plantilla de ADN. También se utilizan en la reparación del ADN y la recombinación genética . [122]
Topoisomerasas y helicasas
Las topoisomerasas son enzimas con actividad tanto nucleasa como ligasa. Estas proteínas cambian la cantidad de superenrollamiento del ADN. Algunas de estas enzimas funcionan cortando la hélice de ADN y permitiendo que una sección gire, reduciendo así su nivel de superenrollamiento; la enzima luego sella la rotura del ADN. [38] Otros tipos de estas enzimas son capaces de cortar una hélice de ADN y luego pasar una segunda hebra de ADN a través de esta ruptura, antes de volver a unirse a la hélice. [123] Las topoisomerasas son necesarias para muchos procesos que involucran al ADN, como la replicación y la transcripción del ADN. [39]
Las helicasas son proteínas que son un tipo de motor molecular . Utilizan la energía química de los nucleósidos trifosfatos , predominantemente trifosfato de adenosina (ATP), para romper los enlaces de hidrógeno entre las bases y desenrollar la doble hélice del ADN en hebras simples. [124] Estas enzimas son esenciales para la mayoría de los procesos en los que las enzimas necesitan acceder a las bases del ADN.
Polimerasas
Las polimerasas son enzimas que sintetizan cadenas de polinucleótidos a partir de nucleósidos trifosfatos . La secuencia de sus productos se crea basándose en cadenas de polinucleótidos existentes, que se denominan plantillas . Estas enzimas funcionan agregando repetidamente un nucleótido al grupo hidroxilo 3 ' al final de la cadena polinucleotídica en crecimiento. Como consecuencia, todas las polimerasas funcionan en una dirección de 5 ′ a 3 ′. [125] En el sitio activo de estas enzimas, los pares de bases de nucleósido trifosfato entrantes a la plantilla: esto permite que las polimerasas sinteticen con precisión la hebra complementaria de su plantilla. Las polimerasas se clasifican según el tipo de plantilla que utilizan.
In DNA replication, DNA-dependent DNA polymerases make copies of DNA polynucleotide chains. To preserve biological information, it is essential that the sequence of bases in each copy are precisely complementary to the sequence of bases in the template strand. Many DNA polymerases have a proofreading activity. Here, the polymerase recognizes the occasional mistakes in the synthesis reaction by the lack of base pairing between the mismatched nucleotides. If a mismatch is detected, a 3′ to 5′ exonuclease activity is activated and the incorrect base removed.[126] In most organisms, DNA polymerases function in a large complex called the replisome that contains multiple accessory subunits, such as the Pinza de ADN o helicasas . [127]
Las ADN polimerasas dependientes de ARN son una clase especializada de polimerasas que copian la secuencia de una cadena de ARN en el ADN. Incluyen la transcriptasa inversa , que es una enzima viral involucrada en la infección de las células por retrovirus , y la telomerasa , que es necesaria para la replicación de los telómeros. [56] [128] Por ejemplo, la transcriptasa inversa del VIH es una enzima para la replicación del virus del SIDA. [128] La telomerasa es una polimerasa inusual porque contiene su propia plantilla de ARN como parte de su estructura. Sintetiza telómerosen los extremos de los cromosomas. Los telómeros evitan la fusión de los extremos de los cromosomas vecinos y protegen los extremos de los cromosomas del daño. [57]
La transcripción se lleva a cabo mediante una ARN polimerasa dependiente de ADN que copia la secuencia de una hebra de ADN en ARN. Para comenzar a transcribir un gen, la ARN polimerasa se une a una secuencia de ADN llamada promotor y separa las hebras de ADN. Luego copia la secuencia del gen en una transcripción de ARN mensajero hasta que alcanza una región de ADN llamada terminador , donde se detiene y se separa del ADN. Al igual que con las ADN polimerasas dependientes de ADN humano, la ARN polimerasa II , la enzima que transcribe la mayoría de los genes en el genoma humano, opera como parte de un gran complejo de proteínas con múltiples subunidades reguladoras y accesorias. [129]
Recombinación genética
A DNA helix usually does not interact with other segments of DNA, and in human cells, the different chromosomes even occupy separate areas in the nucleus called "chromosome territories".[131] This physical separation of different chromosomes is important for the ability of DNA to function as a stable repository for information, as one of the few times chromosomes interact is in chromosomal crossover which occurs during sexual reproduction, when genetic recombination occurs. Chromosomal crossover is when two DNA helices break, swap a section and then rejoin.
La recombinación permite que los cromosomas intercambien información genética y produce nuevas combinaciones de genes, lo que aumenta la eficiencia de la selección natural y puede ser importante en la rápida evolución de nuevas proteínas. [132] La recombinación genética también puede estar involucrada en la reparación del ADN, particularmente en la respuesta de la célula a las roturas de doble hebra. [133]
La forma más común de cruce cromosómico es la recombinación homóloga , donde los dos cromosomas involucrados comparten secuencias muy similares. La recombinación no homóloga puede dañar las células, ya que puede producir translocaciones cromosómicas y anomalías genéticas. La reacción de recombinación es catalizada por enzimas conocidas como recombinasas , como RAD51 . [134] El primer paso en la recombinación es una ruptura de doble hebra causada por una endonucleasa o daño al ADN. [135] Una serie de pasos catalizados en parte por la recombinasa conduce a la unión de las dos hélices mediante al menos una unión de Holliday., en el que un segmento de una sola hebra en cada hélice se hibrida con la hebra complementaria en la otra hélice. La unión de Holliday es una estructura de unión tetraédrica que se puede mover a lo largo del par de cromosomas, intercambiando una hebra por otra. A continuación, la reacción de recombinación se detiene mediante la escisión de la unión y la re-ligación del ADN liberado. [136] Solo hebras de ADN de intercambio de polaridad similar durante la recombinación. Hay dos tipos de hendidura: hendidura este-oeste y hendidura norte-sur. La división norte-sur corta ambas cadenas de ADN, mientras que la división este-oeste tiene una cadena de ADN intacta. La formación de una unión de Holliday durante la recombinación hace posible que la diversidad genética, el intercambio de genes en los cromosomas y la expresión de genomas virales de tipo salvaje.
Evolución
El ADN contiene la información genética que permite que todas las formas de vida funcionen, crezcan y se reproduzcan. Sin embargo, no está claro cuánto tiempo en los 4 mil millones de años de historia de la vida, el ADN ha realizado esta función, ya que se ha propuesto que las primeras formas de vida pueden haber utilizado ARN como su material genético. [137] [138] El ARN puede haber actuado como la parte central del metabolismo celular temprano , ya que puede transmitir información genética y llevar a cabo catálisis como parte de las ribozimas . [139] Este antiguo mundo de ARN donde el ácido nucleico se habría utilizado tanto para la catálisis como para la genética puede haber influido en la evolucióndel código genético actual basado en cuatro bases de nucleótidos. Esto ocurriría, ya que el número de bases diferentes en tal organismo es un compromiso entre un pequeño número de bases que aumentan la precisión de la replicación y un gran número de bases que aumentan la eficacia catalítica de las ribozimas. [140] Sin embargo, no hay evidencia directa de sistemas genéticos antiguos, ya que la recuperación del ADN de la mayoría de los fósiles es imposible porque el ADN sobrevive en el medio ambiente durante menos de un millón de años y se degrada lentamente en pequeños fragmentos en solución. [141] Se han hecho afirmaciones de ADN más antiguo, en particular un informe del aislamiento de una bacteria viable a partir de un cristal de sal de 250 millones de años, [142] pero estas afirmaciones son controvertidas. [143] [144]
Los bloques de construcción de ADN ( adenina , guanina y moléculas orgánicas relacionadas ) pueden haberse formado extraterrestre en el espacio exterior . [145] [146] [147] Los compuestos orgánicos complejos de ADN y ARN de la vida , incluidos el uracilo , la citosina y la timina , también se han formado en el laboratorio en condiciones que imitan las que se encuentran en el espacio exterior , utilizando sustancias químicas iniciales, como pirimidina , encontrado en meteoritos . Pirimidina, como hidrocarburos aromáticos policíclicos(PAH), la sustancia química más rica en carbono que se encuentra en el universo , puede haberse formado en gigantes rojas o en nubes de gas y polvo cósmico interestelar . [148]
En febrero de 2021, los científicos informaron, por primera vez, de la secuenciación de ADN de restos de animales , un mamut en este caso de más de un millón de años, el ADN más antiguo secuenciado hasta la fecha. [149] [150]
Usos en tecnología
Ingeniería genética
Se han desarrollado métodos para purificar el ADN de organismos, como la extracción con fenol-cloroformo , y para manipularlo en el laboratorio, como la digestión de restricción y la reacción en cadena de la polimerasa . La biología y la bioquímica modernas hacen un uso intensivo de estas técnicas en la tecnología del ADN recombinante. El ADN recombinante es una secuencia de ADN artificial que se ha ensamblado a partir de otras secuencias de ADN. Pueden transformarse en organismos en forma de plásmidos o en el formato apropiado, utilizando un vector viral . [151] El genéticamente modificado organisms produced can be used to produce products such as recombinant proteins, used in medical research,[152] or be grown in agriculture.[153][154]
DNA profiling
Los científicos forenses pueden usar el ADN de la sangre , el semen , la piel , la saliva o el cabello que se encuentran en la escena del crimen para identificar un ADN coincidente de un individuo, como un perpetrador. [155] Este proceso se denomina formalmente perfil de ADN , también llamado huella de ADN . En la elaboración de perfiles de ADN, las longitudes de secciones variables de ADN repetitivo, como las repeticiones cortas en tándem y los minisatélites , se comparan entre personas. Este método suele ser una técnica extremadamente confiable para identificar un ADN coincidente. [156]Sin embargo, la identificación puede resultar complicada si la escena está contaminada con ADN de varias personas. [157] La elaboración de perfiles de ADN fue desarrollada en 1984 por el genetista británico Sir Alec Jeffreys , [158] y se utilizó por primera vez en la ciencia forense para condenar a Colin Pitchfork en el caso de asesinatos de Enderby de 1988 . [159]
El desarrollo de la ciencia forense y la capacidad de obtener ahora compatibilidad genética en muestras diminutas de sangre, piel, saliva o cabello ha llevado a volver a examinar muchos casos. Ahora se pueden descubrir pruebas que eran científicamente imposibles en el momento del examen original. Combinado con la eliminación de la ley de doble incriminación en algunos lugares, esto puede permitir la reapertura de casos en los que los juicios anteriores no han producido pruebas suficientes para convencer a un jurado. Es posible que se solicite a las personas acusadas de delitos graves que proporcionen una muestra de ADN para fines de comparación. La defensa más obvia para las coincidencias de ADN obtenidas de forma forense es afirmar que se ha producido una contaminación cruzada de las pruebas. Esto ha resultado en procedimientos meticulosos y estrictos de manejo con nuevos casos de delitos graves.
La elaboración de perfiles de ADN también se utiliza con éxito para identificar positivamente a las víctimas de incidentes con víctimas masivas [160], cuerpos o partes de cuerpos en accidentes graves y víctimas individuales en fosas de guerra masivas, mediante el emparejamiento con miembros de la familia.
El perfil de ADN también se usa en las pruebas de paternidad de ADN para determinar si alguien es el padre biológico o el abuelo de un niño con la probabilidad de que la paternidad sea típicamente del 99,99% cuando el presunto padre está relacionado biológicamente con el niño. Los métodos normales de secuenciación del ADN ocurren después del nacimiento, pero existen nuevos métodos para probar la paternidad mientras la madre aún está embarazada. [161]
Enzimas de ADN o ADN catalítico
Deoxyribozymes, also called DNAzymes or catalytic DNA, were first discovered in 1994.[162] They are mostly single stranded DNA sequences isolated from a large pool of random DNA sequences through a combinatorial approach called in vitro selection or systematic evolution of ligands by exponential enrichment (SELEX). DNAzymes catalyze variety of chemical reactions including RNA-DNA cleavage, RNA-DNA ligation, amino acids phosphorylation-dephosphorylation, carbon-carbon bond formation, etc. DNAzymes can enhance catalytic rate of chemical reactions up to 100,000,000,000-fold over the uncatalyzed reaction.[163]La clase de ADNzimas más estudiada son los tipos de escisión de ARN que se han utilizado para detectar diferentes iones metálicos y diseñar agentes terapéuticos. Se han informado varias ADNzimas específicas de metales, incluida la ADNzima GR-5 (específica del plomo), [162] las ADNzimas CA1-3 (específicas del cobre), [164] la ADNzima 39E (específica de uranilo) y la ADNzima NaA43 ( específico de sodio). [165] La ADNzima NaA43, que se informa que es más de 10.000 veces selectiva para el sodio sobre otros iones metálicos, se utilizó para fabricar un sensor de sodio en tiempo real en las células.
Bioinformática
La bioinformática implica el desarrollo de técnicas para almacenar, extraer datos , buscar y manipular datos biológicos, incluidos los datos de la secuencia de ácidos nucleicos del ADN . Estos han llevado a avances ampliamente aplicados en ciencias de la computación , especialmente algoritmos de búsqueda de cadenas , aprendizaje automático y teoría de bases de datos . [166] Se desarrollaron algoritmos de búsqueda o coincidencia de cadenas, que encuentran una ocurrencia de una secuencia de letras dentro de una secuencia de letras más grande, para buscar secuencias específicas de nucleótidos. [167] La secuencia de ADN puede alinearse con otras secuencias de ADN para identificarsecuencias homólogas y localizar las mutaciones específicas que las hacen distintas. Estas técnicas, especialmente la alineación de secuencias múltiples , se utilizan para estudiar las relaciones filogenéticas y la función de las proteínas. [168] Los conjuntos de datos que representan el valor de secuencias de ADN de genomas completos, como los producidos por el Proyecto Genoma Humano , son difíciles de usar sin las anotaciones que identifican la ubicación de los genes y los elementos reguladores en cada cromosoma. Las regiones de la secuencia de ADN que tienen los patrones característicos asociados con genes que codifican proteínas o ARN pueden identificarse mediante algoritmos de búsqueda de genes , que permiten a los investigadores predecir la presencia de genes específicos.productos genéticos y sus posibles funciones en un organismo incluso antes de que hayan sido aislados experimentalmente. [169] También se pueden comparar genomas completos, lo que puede arrojar luz sobre la historia evolutiva de un organismo en particular y permitir el examen de eventos evolutivos complejos.
Nanotecnología de ADN
DNA nanotechnology uses the unique molecular recognition properties of DNA and other nucleic acids to create self-assembling branched DNA complexes with useful properties.[171] DNA is thus used as a structural material rather than as a carrier of biological information. This has led to the creation of two-dimensional periodic lattices (both tile-based and using the DNA origami method) and three-dimensional structures in the shapes of polyhedra.[172] Nanomechanical devices and algorithmic self-assembly have also been demonstrated,[173] and these DNA structures have been used to template the arrangement of other molecules such as nanopartículas de oro y proteínas estreptavidina . [174]
Historia y antropología
Debido a que el ADN recopila mutaciones a lo largo del tiempo, que luego se heredan, contiene información histórica y, al comparar las secuencias de ADN, los genetistas pueden inferir la historia evolutiva de los organismos, su filogenia . [175] Este campo de la filogenia es una herramienta poderosa en biología evolutiva . Si se comparan las secuencias de ADN dentro de una especie, los genetistas de poblaciones pueden aprender la historia de poblaciones particulares. Esto se puede utilizar en estudios que van desde la genética ecológica hasta la antropología .
Almacenamiento de informacion
El ADN como dispositivo de almacenamiento de información tiene un potencial enorme, ya que tiene una densidad de almacenamiento mucho mayor en comparación con los dispositivos electrónicos. Sin embargo, los altos costos, los tiempos de lectura y escritura lentos ( latencia de la memoria ) y la confiabilidad insuficiente han impedido su uso práctico. [176] [177]
Historia
El ADN fue aislado por primera vez por el médico suizo Friedrich Miescher , quien, en 1869, descubrió una sustancia microscópica en el pus de los vendajes quirúrgicos desechados. Como residía en los núcleos de las células, lo llamó "nucleína". [178] [179] En 1878, Albrecht Kossel aisló el componente no proteico de "nucleína", el ácido nucleico, y luego aisló sus cinco bases nucleicas primarias . [180] [181]
En 1909, Phoebus Levene identificó la unidad de nucleótidos base, azúcar y fosfato del ARN (entonces llamado "ácido nucleico de levadura"). [182] [183] [184] En 1929, Levene identificó el azúcar desoxirribosa en el "ácido nucleico del timo" (ADN). [185] Levene sugirió que el ADN consistía en una cadena de cuatro unidades de nucleótidos unidas entre sí a través de los grupos fosfato ("hipótesis del tetranucleótido"). Levene pensó que la cadena era corta y las bases se repetían en un orden fijo. En 1927, Nikolai Koltsov propuso que los rasgos heredados se heredarían a través de una "molécula hereditaria gigante" formada por "dos hebras de espejo que se replicarían de forma semiconservadora utilizando cada hebra como plantilla".[186] [187]En 1928, Frederick Griffith en su experimento descubrió que los rasgos de la forma "suave" de Pneumococcus podían transferirse a la forma "rugosa" de la misma bacteria mezclando bacterias "lisas" muertas con la forma viva "rugosa". [188] [189] Este sistema proporcionó la primera sugerencia clara de que el ADN transporta información genética.
In 1933, while studying virgin sea urchin eggs, Jean Brachet suggested that DNA is found in the cell nucleus and that RNA is present exclusively in the cytoplasm. At the time, "yeast nucleic acid" (RNA) was thought to occur only in plants, while "thymus nucleic acid" (DNA) only in animals. The latter was thought to be a tetramer, with the function of buffering cellular pH.[190][191]
In 1937, William Astbury produced the first X-ray diffraction patterns that showed that DNA had a regular structure.[192]
En 1943, Oswald Avery , junto con sus colaboradores Colin MacLeod y Maclyn McCarty , identificaron el ADN como el principio transformador , apoyando la sugerencia de Griffith ( experimento de Avery-MacLeod-McCarty ). [193] Erwin Chargaff desarrolló y publicó observaciones ahora conocidas como reglas de Chargaff , indicando que en el ADN de cualquier especie de cualquier organismo, la cantidad de guanina debe ser igual a la citosina y la cantidad de adenina debe ser igual a la timina . [194] [195] A finales de 1951, Francis Crick started working with James Watson at the Cavendish Laboratory within the University of Cambridge. DNA's role in heredity was confirmed in 1952 when Alfred Hershey and Martha Chase in the Hershey–Chase experiment showed that DNA is the genetic material of the enterobacteria phage T2.[196]
En mayo de 1952, Raymond Gosling , un estudiante de posgrado que trabajaba bajo la supervisión de Rosalind Franklin , tomó una imagen de difracción de rayos X , etiquetada como " Foto 51 ", [197] con altos niveles de hidratación del ADN. Esta foto fue entregada a Watson y Crick por Maurice Wilkins y fue fundamental para que obtengan la estructura correcta del ADN. Franklin les dijo a Crick y Watson que la columna vertebral tenía que estar en el exterior. Antes de eso, Linus Pauling, Watson y Crick, tenían modelos erróneos con las cadenas adentro y las bases apuntando hacia afuera. Su identificación del grupo espacial para los cristales de ADN le reveló a Crick que las dos cadenas de ADN eran antiparalelas..[198]
In February 1953, Linus Pauling and Robert Corey proposed a model for nucleic acids containing three intertwined chains, with the phosphates near the axis, and the bases on the outside.[199] Watson and Crick completed their model, which is now accepted as the first correct model of the double-helix of DNA. On 28 February 1953 Crick interrupted patrons' lunchtime at The Eagle pub in Cambridge to announce that he and Watson had "discovered the secret of life".[200]
El número del 25 de abril de 1953 de la revista Nature publicó una serie de cinco artículos que dan el ADN de estructura de doble hélice de Watson y Crick y la evidencia que lo respalda. [201] La estructura se informó en una carta titulada " ESTRUCTURA MOLECULAR DE LOS ÁCIDOS NUCLEICOS Una estructura para el ácido nucleico desoxirribosa ", en la que decían: "No ha pasado inadvertido que el emparejamiento específico que hemos postulado sugiere inmediatamente un posible mecanismo de copia para el material genético ". [9] Esta carta fue seguida por una carta de Franklin y Gosling, que fue la primera publicación de sus propios datos de difracción de rayos X y de su método de análisis original. [42] [202]Luego siguió una carta de Wilkins y dos de sus colegas, que contenía un análisis de patrones de rayos X de ADN-B in vivo , y que respaldaba la presencia in vivo de la estructura de Watson y Crick. [43]
En 1962, después de la muerte de Franklin, Watson, Crick y Wilkins recibieron conjuntamente el Premio Nobel de Fisiología o Medicina . [203] Los premios Nobel se otorgan solo a los beneficiarios vivos. Continúa el debate sobre quién debería recibir crédito por el descubrimiento. [204]
En una influyente presentación en 1957, Crick expuso el dogma central de la biología molecular , que predijo la relación entre el ADN, el ARN y las proteínas, y articuló la "hipótesis del adaptador". [205] La confirmación final del mecanismo de replicación que estaba implícito en la estructura de doble hélice siguió en 1958 a través del experimento Meselson-Stahl . [206] Otros trabajos de Crick y colaboradores mostraron que el código genético se basaba en tripletes de bases que no se superponen, llamados codones , lo que permite a Har Gobind Khorana , Robert W. Holley y Marshall Warren Nirenberg descifrar el código genético. [207]Estos hallazgos representan el nacimiento de la biología molecular . [208]
Ver también
- Autosoma : cualquier cromosoma que no sea un cromosoma sexual
- Comparación de software de simulación de ácidos nucleicos
- Cristalografía : estudio científico de la estructura cristalina
- Día del ADN - Fiesta celebrada el 25 de abril
- Biblioteca química codificada por ADN
- Microarreglo de ADN : colección de manchas de ADN microscópicas adheridas a una superficie sólida
- Trastorno genético : problema de salud causado por una o más anomalías en el genoma
- Genealogía genética : uso de pruebas de ADN en combinación con métodos genealógicos tradicionales para inferir relaciones entre individuos y encontrar ancestros.
- Haplotipo : grupo de genes de uno de los padres
- Meiosis : tipo de división celular en organismos que se reproducen sexualmente y que se utilizan para producir gametos.
- Notación de ácido nucleico: notación universal que utiliza los caracteres romanos A, C, G y T para llamar a los cuatro nucleótidos del ADN.
- Secuencia de ácido nucleico : sucesión de nucleótidos en un ácido nucleico.
- Pangénesis : teoría anterior de que la herencia se basaba en partículas de todas las partes del cuerpo.
- Fosforamidita
- ADN ribosómico
- Southern blot - técnica de análisis de ADN
- Técnicas de dispersión de rayos X
- Ácido xeno nucleico
Referencias
- ^ "ácido desoxirribonucleico" . Diccionario Merriam-Webster .
- ^ Alberts B, Johnson A, Lewis J, Raff M, Roberts K, Walter P (2014). Molecular Biology of the Cell (6th ed.). Garland. p. Chapter 4: DNA, Chromosomes and Genomes. ISBN 978-0-8153-4432-2. Archived from the original on 14 July 2014.
- ^ Purcell A. "DNA". Basic Biology. Archived from the original on 5 January 2017.
- ^ "Uracil". Genome.gov. Retrieved 21 November 2019.
- ^ Russell P (2001). iGenetics. New York: Benjamin Cummings. ISBN 0-8053-4553-1.
- ^ Saenger W (1984). Principles of Nucleic Acid Structure. New York: Springer-Verlag. ISBN 0-387-90762-9.
- ^ a b Alberts B, Johnson A, Lewis J, Raff M, Roberts K, Peter W (2002). Molecular Biology of the Cell (Fourth ed.). New York and London: Garland Science. ISBN 0-8153-3218-1. OCLC 145080076. Archived from the original on 1 November 2016.
- ^ Irobalieva RN, Fogg JM, Catanese DJ, Catanese DJ, Sutthibutpong T, Chen M, Barker AK, Ludtke SJ, Harris SA, Schmid MF, Chiu W, Zechiedrich L (octubre de 2015). "Diversidad estructural del ADN superenrollado" . Comunicaciones de la naturaleza . 6 : 8440. Bibcode : 2015NatCo ... 6.8440I . doi : 10.1038 / ncomms9440 . ISSN 2041-1723 . PMC 4608029 . PMID 26455586 .
- ↑ a b c d Watson JD, Crick FH (abril de 1953). "Estructura molecular de los ácidos nucleicos; una estructura para el ácido nucleico desoxirribosa" (PDF) . Naturaleza . 171 (4356): 737–38. Código Bibliográfico : 1953Natur.171..737W . doi : 10.1038 / 171737a0 . ISSN 0028-0836 . PMID 13054692 . S2CID 4253007 . Archivado (PDF) desde el original el 4 de febrero de 2007.
- ^ Mandelkern M, Elias JG, Eden D, Crothers DM (octubre de 1981). "Las dimensiones del ADN en solución". Revista de Biología Molecular . 152 (1): 153–61. doi : 10.1016 / 0022-2836 (81) 90099-1 . ISSN 0022-2836 . PMID 7338906 .
- ^ Gregory SG, Barlow KF, McLay KE, Kaul R, Swarbreck D, Dunham A, et al. (Mayo de 2006). "La secuencia de ADN y la anotación biológica del cromosoma humano 1" . Naturaleza . 441 (7091): 315–21. Código Bibliográfico : 2006Natur.441..315G . doi : 10.1038 / nature04727 . PMID 16710414 .
- ↑ a b c Berg J, Tymoczko J, Stryer L (2002). Bioquímica . WH Freeman and Company. ISBN 0-7167-4955-6.
- ^ Comisión IUPAC-IUB sobre nomenclatura bioquímica (CBN) (diciembre de 1970). "Abreviaturas y símbolos de ácidos nucleicos, polinucleótidos y sus constituyentes. Recomendaciones 1970" . La revista bioquímica . 120 (3): 449–54. doi : 10.1042 / bj1200449 . ISSN 0306-3283 . PMC 1179624 . PMID 5499957 . Archivado desde el original el 5 de febrero de 2007.
- ↑ a b Ghosh A, Bansal M (abril de 2003). "Un glosario de estructuras de ADN de la A a la Z". Acta Crystallographica Sección D . 59 (Pt 4): 620-26. doi : 10.1107 / S0907444903003251 . ISSN 0907-4449 . PMID 12657780 .
- ^ Creado a partir de PDB 1D65
- ^ Yakovchuk P, Protozanova E, Frank-Kamenetskii MD (2006). "Contribuciones de apilamiento y emparejamiento de bases en la estabilidad térmica de la doble hélice del ADN" . Investigación de ácidos nucleicos . 34 (2): 564–74. doi : 10.1093 / nar / gkj454 . ISSN 0305-1048 . PMC 1360284 . PMID 16449200 .
- ^ Tropp BE (2012). Biología molecular (4ª ed.). Sudbury, Mass .: Jones y Barlett Learning. ISBN 978-0-7637-8663-2.
- ^ Carr S (1953). "Estructura de Watson-Crick del ADN" . Universidad Memorial de Terranova. Archivado desde el original el 19 de julio de 2016 . Consultado el 13 de julio de 2016 .
- ^ Verma S, Eckstein F (1998). "Oligonucleótidos modificados: síntesis y estrategia para usuarios" . Revisión anual de bioquímica . 67 : 99-134. doi : 10.1146 / annurev.biochem.67.1.99 . ISSN 0066-4154 . PMID 9759484 .
- ^ Johnson TB, Coghill RD (1925). "Pirimidinas. CIII. El descubrimiento de la 5-metilcitosina en el ácido tuberculínico, el ácido nucleico del bacilo tuberculoso". Revista de la Sociedad Química Estadounidense . 47 : 2838–44. doi : 10.1021 / ja01688a030 . ISSN 0002-7863 .
- ^ Weigele P, Raleigh EA (octubre de 2016). "Biosíntesis y función de bases modificadas en bacterias y sus virus" . Revisiones químicas . 116 (20): 12655-12687. doi : 10.1021 / acs.chemrev.6b00114 . ISSN 0009-2665 . PMID 27319741 .
- ^ Kumar S, Chinnusamy V, Mohapatra T (2018). "Epigenetics of Modified DNA Bases: 5-Methylcytosine and Beyond". Frontiers in Genetics. 9: 640. doi:10.3389/fgene.2018.00640. ISSN 1664-8021. PMC 6305559. PMID 30619465.
- ^ Carell T, Kurz MQ, Müller M, Rossa M, Spada F (April 2018). "Non-canonical Bases in the Genome: The Regulatory Information Layer in DNA". Angewandte Chemie. 57 (16): 4296–4312. doi:10.1002/anie.201708228. PMID 28941008.
- ^ Wing R, Drew H, Takano T, Broka C, Tanaka S, Itakura K, Dickerson RE (octubre de 1980). "Análisis de la estructura cristalina de una vuelta completa de B-DNA". Naturaleza . 287 (5784): 755–58. Código Bibliográfico : 1980Natur.287..755W . doi : 10.1038 / 287755a0 . PMID 7432492 . S2CID 4315465 .
- ↑ a b Pabo CO, Sauer RT (1984). "Reconocimiento proteína-ADN". Revisión anual de bioquímica . 53 : 293–321. doi : 10.1146 / annurev.bi.53.070184.001453 . PMID 6236744 .
- ^ Nikolova EN, Zhou H, Gottardo FL, Alvey HS, Kimsey IJ, Al-Hashimi HM (2013). "Un relato histórico de los pares de bases de Hoogsteen en el ADN dúplex" . Biopolímeros . 99 (12): 955–68. doi : 10.1002 / bip.22334 . PMC 3844552 . PMID 23818176 .
- ^ Clausen-Schaumann H, Rief M, Tolksdorf C, Gaub HE (abril de 2000). "Estabilidad mecánica de moléculas de ADN individuales" . Revista biofísica . 78 (4): 1997-2007. Código Bibliográfico : 2000BpJ .... 78.1997C . doi : 10.1016 / S0006-3495 (00) 76747-6 . PMC 1300792 . PMID 10733978 .
- ^ Chalikian TV, Völker J, Plum GE, Breslauer KJ (julio de 1999). "Una imagen más unificada para la termodinámica de fusión de dúplex de ácidos nucleicos: una caracterización por técnicas calorimétricas y volumétricas" . Actas de la Academia Nacional de Ciencias de los Estados Unidos de América . 96 (14): 7853–58. Código Bibliográfico : 1999PNAS ... 96.7853C . doi : 10.1073 / pnas.96.14.7853 . PMC 22151 . PMID 10393911 .
- ^ deHaseth PL, Helmann JD (June 1995). "Open complex formation by Escherichia coli RNA polymerase: the mechanism of polymerase-induced strand separation of double helical DNA". Molecular Microbiology. 16 (5): 817–24. doi:10.1111/j.1365-2958.1995.tb02309.x. PMID 7476180. S2CID 24479358.
- ^ Isaksson J, Acharya S, Barman J, Cheruku P, Chattopadhyaya J (diciembre de 2004). "El ADN y el ARN monocatenarios ricos en adenina conservan las características estructurales de sus respectivas conformaciones bicatenarias y muestran diferencias direccionales en el patrón de apilamiento" (PDF) . Bioquímica . 43 (51): 15996–6010. doi : 10.1021 / bi048221v . PMID 15609994 . Archivado (PDF) desde el original el 10 de junio de 2007.
- ^ Designación de las dos hebras de ADN Archivado el 24 de abril de 2008 en Wayback Machine JCBN / NC-IUB Newsletter 1989. Consultado el 7 de mayo de 2008
- ^ Hüttenhofer A, Schattner P, Polacek N (mayo de 2005). "ARN no codificantes: ¿esperanza o exageración?". Tendencias en Genética . 21 (5): 289–97. doi : 10.1016 / j.tig.2005.03.007 . PMID 15851066 .
- ^ Munroe SH (noviembre de 2004). "Diversidad de la regulación antisentido en eucariotas: múltiples mecanismos, patrones emergentes". Revista de bioquímica celular . 93 (4): 664–71. doi : 10.1002 / jcb.20252 . PMID 15389973 . S2CID 23748148 .
- ^ Makalowska I, Lin CF, Makalowski W (February 2005). "Overlapping genes in vertebrate genomes". Computational Biology and Chemistry. 29 (1): 1–12. doi:10.1016/j.compbiolchem.2004.12.006. PMID 15680581.
- ^ Johnson ZI, Chisholm SW (November 2004). "Properties of overlapping genes are conserved across microbial genomes". Genome Research. 14 (11): 2268–72. doi:10.1101/gr.2433104. PMC 525685. PMID 15520290.
- ^ Lamb RA, Horvath CM (agosto de 1991). "Diversidad de estrategias de codificación en virus de influenza" . Tendencias en Genética . 7 (8): 261–66. doi : 10.1016 / 0168-9525 (91) 90326-L . PMC 7173306 . PMID 1771674 .
- ^ Benham CJ, Mielke SP (2005). "Mecánica del ADN" (PDF) . Revisión anual de Ingeniería Biomédica . 7 : 21–53. doi : 10.1146 / annurev.bioeng.6.062403.132016 . PMID 16004565 . S2CID 1427671 . Archivado desde el original (PDF) el 1 de marzo de 2019.
- ↑ a b Champoux JJ (2001). "ADN topoisomerasas: estructura, función y mecanismo" (PDF) . Revisión anual de bioquímica . 70 : 369–413. doi : 10.1146 / annurev.biochem.70.1.369 . PMID 11395412 . S2CID 18144189 .
- ↑ a b Wang JC (junio de 2002). "Roles celulares de ADN topoisomerasas: una perspectiva molecular". Nature Reviews Biología celular molecular . 3 (6): 430–40. doi : 10.1038 / nrm831 . PMID 12042765 . S2CID 205496065 .
- ^ Basu HS, Feuerstein BG, Zarling DA, Shafer RH, Marton LJ (October 1988). "Recognition of Z-RNA and Z-DNA determinants by polyamines in solution: experimental and theoretical studies". Journal of Biomolecular Structure & Dynamics. 6 (2): 299–309. doi:10.1080/07391102.1988.10507714. PMID 2482766.
- ^ Franklin RE, Gosling RG (6 de marzo de 1953). "La estructura de las fibras de timonucleato de sodio I. La influencia del contenido de agua" (PDF) . Acta Crystallogr . 6 (8–9): 673–77. doi : 10.1107 / S0365110X53001939 . Archivado (PDF) desde el original el 9 de enero de 2016.
Franklin RE, Gosling RG (1953). "La estructura de las fibras de timonucleado de sodio. II. La función de Patterson cilíndricamente simétrica" (PDF) . Acta Crystallogr . 6 (8–9): 678–85. doi : 10.1107 / S0365110X53001940 . - ^ a b Franklin RE, Gosling RG (April 1953). "Molecular configuration in sodium thymonucleate" (PDF). Nature. 171 (4356): 740–41. Bibcode:1953Natur.171..740F. doi:10.1038/171740a0. PMID 13054694. S2CID 4268222. Archived (PDF) from the original on 3 January 2011.
- ^ a b Wilkins MH, Stokes AR, Wilson HR (April 1953). "Molecular structure of deoxypentose nucleic acids" (PDF). Nature. 171 (4356): 738–40. Bibcode:1953Natur.171..738W. doi:10.1038/171738a0. PMID 13054693. S2CID 4280080. Archived (PDF) from the original on 13 May 2011.
- ^ Leslie AG, Arnott S, Chandrasekaran R, Ratliff RL (octubre de 1980). "Polimorfismo de dobles hélices de ADN". Revista de Biología Molecular . 143 (1): 49–72. doi : 10.1016 / 0022-2836 (80) 90124-2 . PMID 7441761 .
- ^ Baianu IC (1980). "Orden estructural y desorden parcial en sistemas biológicos" . Toro. Matemáticas. Biol . 42 (4): 137–41. doi : 10.1007 / BF02462372 . S2CID 189888972 .
- ↑ Hosemann R, Bagchi RN (1962). Análisis directo de difracción por materia . Amsterdam - Nueva York: North-Holland Publishers.
- ^ Baianu IC (1978). "X-ray scattering by partially disordered membrane systems" (PDF). Acta Crystallogr A. 34 (5): 751–53. Bibcode:1978AcCrA..34..751B. doi:10.1107/S0567739478001540.
- ^ Wahl MC, Sundaralingam M (1997). "Crystal structures of A-DNA duplexes". Biopolymers. 44 (1): 45–63. doi:10.1002/(SICI)1097-0282(1997)44:1<45::AID-BIP4>3.0.CO;2-#. PMID 9097733.
- ^ Lu XJ, Shakked Z, Olson WK (July 2000). "A-form conformational motifs in ligand-bound DNA structures". Journal of Molecular Biology. 300 (4): 819–40. doi:10.1006/jmbi.2000.3690. PMID 10891271.
- ^ Rothenburg S, Koch-Nolte F, Haag F (December 2001). "DNA methylation and Z-DNA formation as mediators of quantitative differences in the expression of alleles". Immunological Reviews. 184: 286–98. doi:10.1034/j.1600-065x.2001.1840125.x. PMID 12086319. S2CID 20589136.
- ^ Oh DB, Kim YG, Rich A (diciembre de 2002). "Las proteínas de unión al ADN-Z pueden actuar como potentes efectores de la expresión génica in vivo" . Actas de la Academia Nacional de Ciencias de los Estados Unidos de América . 99 (26): 16666–71. Código bibliográfico : 2002PNAS ... 9916666O . doi : 10.1073 / pnas.262672699 . PMC 139201 . PMID 12486233 .
- ^ Palmer J (2 de diciembre de 2010). "Las bacterias amantes del arsénico pueden ayudar en la búsqueda de vida extraterrestre" . BBC News . Archivado desde el original el 3 de diciembre de 2010 . Consultado el 2 de diciembre de 2010 .
- ↑ a b Bortman H (2 de diciembre de 2010). "Las bacterias que comen arsénico abren nuevas posibilidades para la vida alienígena" . Space.com . Archivado desde el original el 4 de diciembre de 2010 . Consultado el 2 de diciembre de 2010 .
- ^ Katsnelson A (2 de diciembre de 2010). "El microbio que come arsénico puede redefinir la química de la vida" . Nature News . doi : 10.1038 / news.2010.645 . Archivado desde el original el 12 de febrero de 2012.
- ^ Cressey D (3 de octubre de 2012). " La bacteria ' arsénico-vida' prefiere fósforo después de todo". Nature News . doi : 10.1038 / nature.2012.11520 . S2CID 87341731 .
- ↑ a b Greider CW, Blackburn EH (diciembre de 1985). "Identificación de una actividad transferasa terminal de telómero específica en extractos de Tetrahymena" . Celular . 43 (2 Pt 1): 405-13. doi : 10.1016 / 0092-8674 (85) 90170-9 . PMID 3907856 .
- ↑ a b c Nugent CI, Lundblad V (abril de 1998). "La telomerasa transcriptasa inversa: componentes y regulación" . Genes y desarrollo . 12 (8): 1073–85. doi : 10.1101 / gad.12.8.1073 . PMID 9553037 .
- ^ Wright WE, Tesmer VM, Huffman KE, Levene SD, Shay JW (noviembre de 1997). "Los cromosomas humanos normales tienen largos salientes teloméricos ricos en G en un extremo" . Genes y desarrollo . 11 (21): 2801-09. doi : 10.1101 / gad.11.21.2801 . PMC 316649 . PMID 9353250 .
- ^ Creado a partir de Archivado el 17 de octubre de 2016 en Wayback Machine.
- ↑ a b Burge S, Parkinson GN, Hazel P, Todd AK, Neidle S (2006). "ADN cuádruple: secuencia, topología y estructura" . Investigación de ácidos nucleicos . 34 (19): 5402-15. doi : 10.1093 / nar / gkl655 . PMC 1636468 . PMID 17012276 .
- ^ Parkinson GN, Lee MP, Neidle S (junio de 2002). "Estructura cristalina de cuadruplex paralelos de ADN telomérico humano". Naturaleza . 417 (6891): 876–80. Código Bibliográfico : 2002Natur.417..876P . doi : 10.1038 / nature755 . PMID 12050675 . S2CID 4422211 .
- ^ Griffith JD, Comeau L, Rosenfield S, Stansel RM, Bianchi A, Moss H, de Lange T (mayo de 1999). "Telómeros de mamíferos terminan en un gran bucle dúplex". Celular . 97 (4): 503-14. CiteSeerX 10.1.1.335.2649 . doi : 10.1016 / S0092-8674 (00) 80760-6 . PMID 10338214 . S2CID 721901 .
- ^ Seeman NC (noviembre de 2005). "El ADN permite el control a nanoescala de la estructura de la materia" . Reseñas trimestrales de biofísica . 38 (4): 363–71. doi : 10.1017 / S0033583505004087 . PMC 3478329 . PMID 16515737 .
- ^ Warren M (21 de febrero de 2019). "Cuatro nuevas letras de ADN doblan el alfabeto de la vida" . Naturaleza . 566 (7745): 436. Bibcode : 2019Natur.566..436W . doi : 10.1038 / d41586-019-00650-8 . PMID 30809059 .
- ^ Hoshika S, Leal NA, Kim MJ, Kim MS, Karalkar NB, Kim HJ, et al. (22 February 2019). "Hachimoji DNA and RNA: A genetic system with eight building blocks (paywall)". Science. 363 (6429): 884–887. Bibcode:2019Sci...363..884H. doi:10.1126/science.aat0971. PMC 6413494. PMID 30792304.
- ^ Burghardt B, Hartmann AK (febrero de 2007). "Diseño de estructura secundaria de ARN" . Revisión E física . 75 (2): 021920. arXiv : física / 0609135 . Código bibliográfico : 2007PhRvE..75b1920B . doi : 10.1103 / PhysRevE.75.021920 . PMID 17358380 . S2CID 17574854 .
- ^ Hu Q, Rosenfeld MG (2012). "Epigenetic regulation of human embryonic stem cells". Frontiers in Genetics. 3: 238. doi:10.3389/fgene.2012.00238. PMC 3488762. PMID 23133442.
- ^ Klose RJ, Bird AP (February 2006). "Genomic DNA methylation: the mark and its mediators". Trends in Biochemical Sciences. 31 (2): 89–97. doi:10.1016/j.tibs.2005.12.008. PMID 16403636.
- ^ Bird A (January 2002). "DNA methylation patterns and epigenetic memory". Genes & Development. 16 (1): 6–21. doi:10.1101/gad.947102. PMID 11782440.
- ^ Walsh CP, Xu GL (2006). "Cytosine methylation and DNA repair". Current Topics in Microbiology and Immunology. 301: 283–315. doi:10.1007/3-540-31390-7_11. ISBN 3-540-29114-8. PMID 16570853.
- ^ Kriaucionis S, Heintz N (May 2009). "The nuclear DNA base 5-hydroxymethylcytosine is present in Purkinje neurons and the brain". Science. 324 (5929): 929–30. Bibcode:2009Sci...324..929K. doi:10.1126/science.1169786. PMC 3263819. PMID 19372393.
- ^ Ratel D, Ravanat JL, Berger F, Wion D (March 2006). "N6-methyladenine: the other methylated base of DNA". BioEssays. 28 (3): 309–15. doi:10.1002/bies.20342. PMC 2754416. PMID 16479578.
- ^ Gommers-Ampt JH, Van Leeuwen F, de Beer AL, Vliegenthart JF, Dizdaroglu M, Kowalak JA, Crain PF, Borst P (December 1993). "beta-D-glucosyl-hydroxymethyluracil: a novel modified base present in the DNA of the parasitic protozoan T. brucei". Cell. 75 (6): 1129–36. doi:10.1016/0092-8674(93)90322-H. hdl:1874/5219. PMID 8261512. S2CID 24801094.
- ^ Created from PDB 1JDG Archived 22 September 2008 at the Wayback Machine
- ^ Douki T, Reynaud-Angelin A, Cadet J, Sage E (August 2003). "Bipyrimidine photoproducts rather than oxidative lesions are the main type of DNA damage involved in the genotoxic effect of solar UVA radiation". Biochemistry. 42 (30): 9221–26. doi:10.1021/bi034593c. PMID 12885257.
- ^ Cadet J, Delatour T, Douki T, Gasparutto D, Pouget JP, Ravanat JL, Sauvaigo S (March 1999). "Hydroxyl radicals and DNA base damage". Mutation Research. 424 (1–2): 9–21. doi:10.1016/S0027-5107(99)00004-4. PMID 10064846.
- ^ Beckman KB, Ames BN (August 1997). "Oxidative decay of DNA". The Journal of Biological Chemistry. 272 (32): 19633–36. doi:10.1074/jbc.272.32.19633. PMID 9289489.
- ^ Valerie K, Povirk LF (September 2003). "Regulation and mechanisms of mammalian double-strand break repair". Oncogene. 22 (37): 5792–812. doi:10.1038/sj.onc.1206679. PMID 12947387.
- ^ Johnson G (28 December 2010). "Unearthing Prehistoric Tumors, and Debate". The New York Times. Archived from the original on 24 June 2017.
If we lived long enough, sooner or later we all would get cancer.
- ^ Alberts B, Johnson A, Lewis J, et al. (2002). "The Preventable Causes of Cancer". Molecular biology of the cell (4th ed.). New York: Garland Science. ISBN 0-8153-4072-9. Archived from the original on 2 January 2016.
A certain irreducible background incidence of cancer is to be expected regardless of circumstances: mutations can never be absolutely avoided, because they are an inescapable consequence of fundamental limitations on the accuracy of DNA replication, as discussed in Chapter 5. If a human could live long enough, it is inevitable that at least one of his or her cells would eventually accumulate a set of mutations sufficient for cancer to develop.
- ^ Bernstein H, Payne CM, Bernstein C, Garewal H, Dvorak K (2008). "Cancer and aging as consequences of un-repaired DNA damage". In Kimura H, Suzuki A (eds.). New Research on DNA Damage. New York: Nova Science Publishers. pp. 1–47. ISBN 978-1-60456-581-2. Archived from the original on 25 October 2014.
- ^ Hoeijmakers JH (October 2009). "DNA damage, aging, and cancer". The New England Journal of Medicine. 361 (15): 1475–85. doi:10.1056/NEJMra0804615. PMID 19812404.
- ^ Freitas AA, de Magalhães JP (2011). "A review and appraisal of the DNA damage theory of ageing". Mutation Research. 728 (1–2): 12–22. doi:10.1016/j.mrrev.2011.05.001. PMID 21600302.
- ^ Ferguson LR, Denny WA (September 1991). "The genetic toxicology of acridines". Mutation Research. 258 (2): 123–60. doi:10.1016/0165-1110(91)90006-H. PMID 1881402.
- ^ Stephens TD, Bunde CJ, Fillmore BJ (June 2000). "Mechanism of action in thalidomide teratogenesis". Biochemical Pharmacology. 59 (12): 1489–99. doi:10.1016/S0006-2952(99)00388-3. PMID 10799645.
- ^ Jeffrey AM (1985). "DNA modification by chemical carcinogens". Pharmacology & Therapeutics. 28 (2): 237–72. doi:10.1016/0163-7258(85)90013-0. PMID 3936066.
- ^ Braña MF, Cacho M, Gradillas A, de Pascual-Teresa B, Ramos A (November 2001). "Intercalators as anticancer drugs". Current Pharmaceutical Design. 7 (17): 1745–80. doi:10.2174/1381612013397113. PMID 11562309.
- ^ Venter JC, Adams MD, Myers EW, Li PW, Mural RJ, Sutton GG, et al. (February 2001). "The sequence of the human genome". Science. 291 (5507): 1304–51. Bibcode:2001Sci...291.1304V. doi:10.1126/science.1058040. PMID 11181995.
- ^ Thanbichler M, Wang SC, Shapiro L (October 2005). "The bacterial nucleoid: a highly organized and dynamic structure". Journal of Cellular Biochemistry. 96 (3): 506–21. doi:10.1002/jcb.20519. PMID 15988757.
- ^ Wolfsberg TG, McEntyre J, Schuler GD (February 2001). "Guide to the draft human genome". Nature. 409 (6822): 824–26. Bibcode:2001Natur.409..824W. doi:10.1038/35057000. PMID 11236998.
- ^ Gregory TR (January 2005). "The C-value enigma in plants and animals: a review of parallels and an appeal for partnership". Annals of Botany. 95 (1): 133–46. doi:10.1093/aob/mci009. PMC 4246714. PMID 15596463.
- ^ Birney E, Stamatoyannopoulos JA, Dutta A, Guigó R, Gingeras TR, Margulies EH, et al. (June 2007). "Identification and analysis of functional elements in 1% of the human genome by the ENCODE pilot project". Nature. 447 (7146): 799–816. Bibcode:2007Natur.447..799B. doi:10.1038/nature05874. PMC 2212820. PMID 17571346.
- ^ Created from PDB 1MSW Archived 6 January 2008 at the Wayback Machine
- ^ Pidoux AL, Allshire RC (March 2005). "The role of heterochromatin in centromere function". Philosophical Transactions of the Royal Society of London. Series B, Biological Sciences. 360 (1455): 569–79. doi:10.1098/rstb.2004.1611. PMC 1569473. PMID 15905142.
- ^ Harrison PM, Hegyi H, Balasubramanian S, Luscombe NM, Bertone P, Echols N, Johnson T, Gerstein M (February 2002). "Molecular fossils in the human genome: identification and analysis of the pseudogenes in chromosomes 21 and 22". Genome Research. 12 (2): 272–80. doi:10.1101/gr.207102. PMC 155275. PMID 11827946.
- ^ Harrison PM, Gerstein M (May 2002). "Studying genomes through the aeons: protein families, pseudogenes and proteome evolution". Journal of Molecular Biology. 318 (5): 1155–74. doi:10.1016/S0022-2836(02)00109-2. PMID 12083509.
- ^ Albà M (2001). "Replicative DNA polymerases". Genome Biology. 2 (1): REVIEWS3002. doi:10.1186/gb-2001-2-1-reviews3002. PMC 150442. PMID 11178285.
- ^ Tani K, Nasu M (2010). "Roles of Extracellular DNA in Bacterial Ecosystems". In Kikuchi Y, Rykova EY (eds.). Extracellular Nucleic Acids. Springer. pp. 25–38. ISBN 978-3-642-12616-1.
- ^ Vlassov VV, Laktionov PP, Rykova EY (July 2007). "Extracellular nucleic acids". BioEssays. 29 (7): 654–67. doi:10.1002/bies.20604. PMID 17563084. S2CID 32463239.
- ^ Finkel SE, Kolter R (November 2001). "DNA as a nutrient: novel role for bacterial competence gene homologs". Journal of Bacteriology. 183 (21): 6288–93. doi:10.1128/JB.183.21.6288-6293.2001. PMC 100116. PMID 11591672.
- ^ Mulcahy H, Charron-Mazenod L, Lewenza S (November 2008). "Extracellular DNA chelates cations and induces antibiotic resistance in Pseudomonas aeruginosa biofilms". PLOS Pathogens. 4 (11): e1000213. doi:10.1371/journal.ppat.1000213. PMC 2581603. PMID 19023416.
- ^ Berne C, Kysela DT, Brun YV (August 2010). "A bacterial extracellular DNA inhibits settling of motile progeny cells within a biofilm". Molecular Microbiology. 77 (4): 815–29. doi:10.1111/j.1365-2958.2010.07267.x. PMC 2962764. PMID 20598083.
- ^ Whitchurch CB, Tolker-Nielsen T, Ragas PC, Mattick JS (February 2002). "Extracellular DNA required for bacterial biofilm formation". Science. 295 (5559): 1487. doi:10.1126/science.295.5559.1487. PMID 11859186.
- ^ Hu W, Li L, Sharma S, Wang J, McHardy I, Lux R, Yang Z, He X, Gimzewski JK, Li Y, Shi W (2012). "DNA builds and strengthens the extracellular matrix in Myxococcus xanthus biofilms by interacting with exopolysaccharides". PLOS ONE. 7 (12): e51905. Bibcode:2012PLoSO...751905H. doi:10.1371/journal.pone.0051905. PMC 3530553. PMID 23300576.
- ^ Hui L, Bianchi DW (February 2013). "Recent advances in the prenatal interrogation of the human fetal genome". Trends in Genetics. 29 (2): 84–91. doi:10.1016/j.tig.2012.10.013. PMC 4378900. PMID 23158400.
- ^ Foote AD, Thomsen PF, Sveegaard S, Wahlberg M, Kielgast J, Kyhn LA, et al. (2012). "Investigating the potential use of environmental DNA (eDNA) for genetic monitoring of marine mammals". PLOS ONE. 7 (8): e41781. Bibcode:2012PLoSO...741781F. doi:10.1371/journal.pone.0041781. PMC 3430683. PMID 22952587.
- ^ "Researchers Detect Land Animals Using DNA in Nearby Water Bodies".
- ^ Sandman K, Pereira SL, Reeve JN (December 1998). "Diversity of prokaryotic chromosomal proteins and the origin of the nucleosome". Cellular and Molecular Life Sciences. 54 (12): 1350–64. doi:10.1007/s000180050259. PMID 9893710. S2CID 21101836.
- ^ Dame RT (May 2005). "The role of nucleoid-associated proteins in the organization and compaction of bacterial chromatin". Molecular Microbiology. 56 (4): 858–70. doi:10.1111/j.1365-2958.2005.04598.x. PMID 15853876. S2CID 26965112.
- ^ Luger K, Mäder AW, Richmond RK, Sargent DF, Richmond TJ (September 1997). "Crystal structure of the nucleosome core particle at 2.8 A resolution". Nature. 389 (6648): 251–60. Bibcode:1997Natur.389..251L. doi:10.1038/38444. PMID 9305837. S2CID 4328827.
- ^ Jenuwein T, Allis CD (August 2001). "Translating the histone code" (PDF). Science. 293 (5532): 1074–80. doi:10.1126/science.1063127. PMID 11498575. S2CID 1883924. Archived (PDF) from the original on 8 August 2017.
- ^ Ito T (2003). "Nucleosome assembly and remodeling". Current Topics in Microbiology and Immunology. 274: 1–22. doi:10.1007/978-3-642-55747-7_1. ISBN 978-3-540-44208-0. PMID 12596902.
- ^ Thomas JO (August 2001). "HMG1 and 2: architectural DNA-binding proteins". Biochemical Society Transactions. 29 (Pt 4): 395–401. doi:10.1042/BST0290395. PMID 11497996.
- ^ Grosschedl R, Giese K, Pagel J (March 1994). "HMG domain proteins: architectural elements in the assembly of nucleoprotein structures". Trends in Genetics. 10 (3): 94–100. doi:10.1016/0168-9525(94)90232-1. PMID 8178371.
- ^ Iftode C, Daniely Y, Borowiec JA (1999). "Replication protein A (RPA): the eukaryotic SSB". Critical Reviews in Biochemistry and Molecular Biology. 34 (3): 141–80. doi:10.1080/10409239991209255. PMID 10473346.
- ^ Created from PDB 1LMB Archived 6 January 2008 at the Wayback Machine
- ^ Myers LC, Kornberg RD (2000). "Mediator of transcriptional regulation". Annual Review of Biochemistry. 69: 729–49. doi:10.1146/annurev.biochem.69.1.729. PMID 10966474.
- ^ Spiegelman BM, Heinrich R (October 2004). "Biological control through regulated transcriptional coactivators". Cell. 119 (2): 157–67. doi:10.1016/j.cell.2004.09.037. PMID 15479634.
- ^ Li Z, Van Calcar S, Qu C, Cavenee WK, Zhang MQ, Ren B (July 2003). "A global transcriptional regulatory role for c-Myc in Burkitt's lymphoma cells". Proceedings of the National Academy of Sciences of the United States of America. 100 (14): 8164–69. Bibcode:2003PNAS..100.8164L. doi:10.1073/pnas.1332764100. PMC 166200. PMID 12808131.
- ^ Created from PDB 1RVA Archived 6 January 2008 at the Wayback Machine
- ^ Bickle TA, Krüger DH (June 1993). "Biology of DNA restriction". Microbiological Reviews. 57 (2): 434–50. doi:10.1128/MMBR.57.2.434-450.1993. PMC 372918. PMID 8336674.
- ^ a b Doherty AJ, Suh SW (November 2000). "Structural and mechanistic conservation in DNA ligases". Nucleic Acids Research. 28 (21): 4051–58. doi:10.1093/nar/28.21.4051. PMC 113121. PMID 11058099.
- ^ Schoeffler AJ, Berger JM (December 2005). "Recent advances in understanding structure-function relationships in the type II topoisomerase mechanism". Biochemical Society Transactions. 33 (Pt 6): 1465–70. doi:10.1042/BST20051465. PMID 16246147.
- ^ Tuteja N, Tuteja R (May 2004). "Unraveling DNA helicases. Motif, structure, mechanism and function" (PDF). European Journal of Biochemistry. 271 (10): 1849–63. doi:10.1111/j.1432-1033.2004.04094.x. PMID 15128295.
- ^ Joyce CM, Steitz TA (November 1995). "Polymerase structures and function: variations on a theme?". Journal of Bacteriology. 177 (22): 6321–29. doi:10.1128/jb.177.22.6321-6329.1995. PMC 177480. PMID 7592405.
- ^ Hubscher U, Maga G, Spadari S (2002). "Eukaryotic DNA polymerases" (PDF). Annual Review of Biochemistry. 71: 133–63. doi:10.1146/annurev.biochem.71.090501.150041. PMID 12045093. S2CID 26171993. Archived from the original (PDF) on 26 January 2021.
- ^ Johnson A, O'Donnell M (2005). "Cellular DNA replicases: components and dynamics at the replication fork". Annual Review of Biochemistry. 74: 283–315. doi:10.1146/annurev.biochem.73.011303.073859. PMID 15952889.
- ^ a b Tarrago-Litvak L, Andréola ML, Nevinsky GA, Sarih-Cottin L, Litvak S (May 1994). "The reverse transcriptase of HIV-1: from enzymology to therapeutic intervention". FASEB Journal. 8 (8): 497–503. doi:10.1096/fasebj.8.8.7514143. PMID 7514143. S2CID 39614573.
- ^ Martinez E (December 2002). "Multi-protein complexes in eukaryotic gene transcription". Plant Molecular Biology. 50 (6): 925–47. doi:10.1023/A:1021258713850. PMID 12516863. S2CID 24946189.
- ^ Created from PDB 1M6G Archived 10 January 2010 at the Wayback Machine
- ^ Cremer T, Cremer C (April 2001). "Chromosome territories, nuclear architecture and gene regulation in mammalian cells". Nature Reviews Genetics. 2 (4): 292–301. doi:10.1038/35066075. PMID 11283701. S2CID 8547149.
- ^ Pál C, Papp B, Lercher MJ (May 2006). "An integrated view of protein evolution". Nature Reviews Genetics. 7 (5): 337–48. doi:10.1038/nrg1838. PMID 16619049. S2CID 23225873.
- ^ O'Driscoll M, Jeggo PA (January 2006). "The role of double-strand break repair – insights from human genetics". Nature Reviews Genetics. 7 (1): 45–54. doi:10.1038/nrg1746. PMID 16369571. S2CID 7779574.
- ^ Vispé S, Defais M (October 1997). "Mammalian Rad51 protein: a RecA homologue with pleiotropic functions". Biochimie. 79 (9–10): 587–92. doi:10.1016/S0300-9084(97)82007-X. PMID 9466696.
- ^ Neale MJ, Keeney S (July 2006). "Clarifying the mechanics of DNA strand exchange in meiotic recombination". Nature. 442 (7099): 153–58. Bibcode:2006Natur.442..153N. doi:10.1038/nature04885. PMC 5607947. PMID 16838012.
- ^ Dickman MJ, Ingleston SM, Sedelnikova SE, Rafferty JB, Lloyd RG, Grasby JA, Hornby DP (November 2002). "The RuvABC resolvasome". European Journal of Biochemistry. 269 (22): 5492–501. doi:10.1046/j.1432-1033.2002.03250.x. PMID 12423347. S2CID 39505263.
- ^ Joyce GF (July 2002). "The antiquity of RNA-based evolution". Nature. 418 (6894): 214–21. Bibcode:2002Natur.418..214J. doi:10.1038/418214a. PMID 12110897. S2CID 4331004.
- ^ Orgel LE (2004). "Prebiotic chemistry and the origin of the RNA world". Critical Reviews in Biochemistry and Molecular Biology. 39 (2): 99–123. CiteSeerX 10.1.1.537.7679. doi:10.1080/10409230490460765. PMID 15217990.
- ^ Davenport RJ (May 2001). "Ribozymes. Making copies in the RNA world". Science. 292 (5520): 1278a–1278. doi:10.1126/science.292.5520.1278a. PMID 11360970. S2CID 85976762.
- ^ Szathmáry E (April 1992). "What is the optimum size for the genetic alphabet?". Proceedings of the National Academy of Sciences of the United States of America. 89 (7): 2614–18. Bibcode:1992PNAS...89.2614S. doi:10.1073/pnas.89.7.2614. PMC 48712. PMID 1372984.
- ^ Lindahl T (April 1993). "Instability and decay of the primary structure of DNA". Nature. 362 (6422): 709–15. Bibcode:1993Natur.362..709L. doi:10.1038/362709a0. PMID 8469282. S2CID 4283694.
- ^ Vreeland RH, Rosenzweig WD, Powers DW (October 2000). "Isolation of a 250 million-year-old halotolerant bacterium from a primary salt crystal". Nature. 407 (6806): 897–900. Bibcode:2000Natur.407..897V. doi:10.1038/35038060. PMID 11057666. S2CID 9879073.
- ^ Hebsgaard MB, Phillips MJ, Willerslev E (May 2005). "Geologically ancient DNA: fact or artefact?". Trends in Microbiology. 13 (5): 212–20. doi:10.1016/j.tim.2005.03.010. PMID 15866038.
- ^ Nickle DC, Learn GH, Rain MW, Mullins JI, Mittler JE (January 2002). "Curiously modern DNA for a "250 million-year-old" bacterium". Journal of Molecular Evolution. 54 (1): 134–37. Bibcode:2002JMolE..54..134N. doi:10.1007/s00239-001-0025-x. PMID 11734907. S2CID 24740859.
- ^ Callahan MP, Smith KE, Cleaves HJ, Ruzicka J, Stern JC, Glavin DP, House CH, Dworkin JP (August 2011). "Carbonaceous meteorites contain a wide range of extraterrestrial nucleobases". Proceedings of the National Academy of Sciences of the United States of America. 108 (34): 13995–98. Bibcode:2011PNAS..10813995C. doi:10.1073/pnas.1106493108. PMC 3161613. PMID 21836052.
- ^ Steigerwald J (8 August 2011). "NASA Researchers: DNA Building Blocks Can Be Made in Space". NASA. Archived from the original on 23 June 2015. Retrieved 10 August 2011.
- ^ ScienceDaily Staff (9 August 2011). "DNA Building Blocks Can Be Made in Space, NASA Evidence Suggests". ScienceDaily. Archived from the original on 5 September 2011. Retrieved 9 August 2011.
- ^ Marlaire R (3 March 2015). "NASA Ames Reproduces the Building Blocks of Life in Laboratory". NASA. Archived from the original on 5 March 2015. Retrieved 5 March 2015.
- ^ Hunt, Katie (17 February 2021). "World's oldest DNA sequenced from a mammoth that lived more than a million years ago". CNN News. Retrieved 17 February 2021.
- ^ Callaway, Ewen (17 February 2021). "Million-year-old mammoth genomes shatter record for oldest ancient DNA - Permafrost-preserved teeth, up to 1.6 million years old, identify a new kind of mammoth in Siberia". Nature. 590 (7847): 537–538. doi:10.1038/d41586-021-00436-x. PMID 33597786.
- ^ Goff SP, Berg P (December 1976). "Construction of hybrid viruses containing SV40 and lambda phage DNA segments and their propagation in cultured monkey cells". Cell. 9 (4 PT 2): 695–705. doi:10.1016/0092-8674(76)90133-1. PMID 189942. S2CID 41788896.
- ^ Houdebine LM (2007). "Transgenic animal models in biomedical research". Target Discovery and Validation Reviews and Protocols. Methods in Molecular Biology. 360. pp. 163–202. doi:10.1385/1-59745-165-7:163. ISBN 978-1-59745-165-9. PMID 17172731.
- ^ Daniell H, Dhingra A (April 2002). "Multigene engineering: dawn of an exciting new era in biotechnology". Current Opinion in Biotechnology. 13 (2): 136–41. doi:10.1016/S0958-1669(02)00297-5. PMC 3481857. PMID 11950565.
- ^ Job D (November 2002). "Plant biotechnology in agriculture". Biochimie. 84 (11): 1105–10. doi:10.1016/S0300-9084(02)00013-5. PMID 12595138.
- ^ Curtis C, Hereward J (29 August 2017). "From the crime scene to the courtroom: the journey of a DNA sample". The Conversation. Archived from the original on 22 October 2017. Retrieved 22 October 2017.
- ^ Collins A, Morton NE (June 1994). "Likelihood ratios for DNA identification". Proceedings of the National Academy of Sciences of the United States of America. 91 (13): 6007–11. Bibcode:1994PNAS...91.6007C. doi:10.1073/pnas.91.13.6007. PMC 44126. PMID 8016106.
- ^ Weir BS, Triggs CM, Starling L, Stowell LI, Walsh KA, Buckleton J (March 1997). "Interpreting DNA mixtures" (PDF). Journal of Forensic Sciences. 42 (2): 213–22. doi:10.1520/JFS14100J. PMID 9068179. S2CID 14511630.
- ^ Jeffreys AJ, Wilson V, Thein SL (1985). "Individual-specific 'fingerprints' of human DNA". Nature. 316 (6023): 76–79. Bibcode:1985Natur.316...76J. doi:10.1038/316076a0. PMID 2989708. S2CID 4229883.
- ^ Colin Pitchfork – first murder conviction on DNA evidence also clears the prime suspect Forensic Science Service Accessed 23 December 2006
- ^ "DNA Identification in Mass Fatality Incidents". National Institute of Justice. September 2006. Archived from the original on 12 November 2006.
- ^ "Paternity Blood Tests That Work Early in a Pregnancy" New York Times June 20, 2012 Archived 24 June 2017 at the Wayback Machine
- ^ a b Breaker RR, Joyce GF (December 1994). "A DNA enzyme that cleaves RNA". Chemistry & Biology. 1 (4): 223–29. doi:10.1016/1074-5521(94)90014-0. PMID 9383394.
- ^ Chandra M, Sachdeva A, Silverman SK (October 2009). "DNA-catalyzed sequence-specific hydrolysis of DNA". Nature Chemical Biology. 5 (10): 718–20. doi:10.1038/nchembio.201. PMC 2746877. PMID 19684594.
- ^ Carmi N, Shultz LA, Breaker RR (December 1996). "In vitro selection of self-cleaving DNAs". Chemistry & Biology. 3 (12): 1039–46. doi:10.1016/S1074-5521(96)90170-2. PMID 9000012.
- ^ Torabi SF, Wu P, McGhee CE, Chen L, Hwang K, Zheng N, Cheng J, Lu Y (May 2015). "In vitro selection of a sodium-specific DNAzyme and its application in intracellular sensing". Proceedings of the National Academy of Sciences of the United States of America. 112 (19): 5903–08. Bibcode:2015PNAS..112.5903T. doi:10.1073/pnas.1420361112. PMC 4434688. PMID 25918425.
- ^ Baldi P, Brunak S (2001). Bioinformatics: The Machine Learning Approach. MIT Press. ISBN 978-0-262-02506-5. OCLC 45951728.
- ^ Gusfield D (15 January 1997). Algorithms on Strings, Trees, and Sequences: Computer Science and Computational Biology. Cambridge University Press. ISBN 978-0-521-58519-4.
- ^ Sjölander K (January 2004). "Phylogenomic inference of protein molecular function: advances and challenges". Bioinformatics. 20 (2): 170–79. CiteSeerX 10.1.1.412.943. doi:10.1093/bioinformatics/bth021. PMID 14734307.
- ^ Mount DM (2004). Bioinformatics: Sequence and Genome Analysis (2nd ed.). Cold Spring Harbor, NY: Cold Spring Harbor Laboratory Press. ISBN 0-87969-712-1. OCLC 55106399.
- ^ Strong, Michael (2004). "Protein Nanomachines". PLOS Biology. 2 (3): e73. doi:10.1371/journal.pbio.0020073. PMC 368168. PMID 15024422. S2CID 13222080.
- ^ Rothemund PW (March 2006). "Folding DNA to create nanoscale shapes and patterns" (PDF). Nature. 440 (7082): 297–302. Bibcode:2006Natur.440..297R. doi:10.1038/nature04586. PMID 16541064. S2CID 4316391.
- ^ Andersen ES, Dong M, Nielsen MM, Jahn K, Subramani R, Mamdouh W, Golas MM, Sander B, Stark H, Oliveira CL, Pedersen JS, Birkedal V, Besenbacher F, Gothelf KV, Kjems J (May 2009). "Self-assembly of a nanoscale DNA box with a controllable lid". Nature. 459 (7243): 73–76. Bibcode:2009Natur.459...73A. doi:10.1038/nature07971. hdl:11858/00-001M-0000-0010-9362-B. PMID 19424153. S2CID 4430815.
- ^ Ishitsuka Y, Ha T (May 2009). "DNA nanotechnology: a nanomachine goes live". Nature Nanotechnology. 4 (5): 281–82. Bibcode:2009NatNa...4..281I. doi:10.1038/nnano.2009.101. PMID 19421208.
- ^ Aldaye FA, Palmer AL, Sleiman HF (September 2008). "Assembling materials with DNA as the guide". Science. 321 (5897): 1795–99. Bibcode:2008Sci...321.1795A. doi:10.1126/science.1154533. PMID 18818351. S2CID 2755388.
- ^ Wray GA (2002). "Dating branches on the tree of life using DNA". Genome Biology. 3 (1): REVIEWS0001. doi:10.1186/gb-2001-3-1-reviews0001. PMC 150454. PMID 11806830.
- ^ Panda D, Molla KA, Baig MJ, Swain A, Behera D, Dash M (May 2018). "DNA as a digital information storage device: hope or hype?". 3 Biotech. 8 (5): 239. doi:10.1007/s13205-018-1246-7. PMC 5935598. PMID 29744271.
- ^ Akram F, Haq IU, Ali H, Laghari AT (October 2018). "Trends to store digital data in DNA: an overview". Molecular Biology Reports. 45 (5): 1479–1490. doi:10.1007/s11033-018-4280-y. PMID 30073589. S2CID 51905843.
- ^ Miescher F (1871). "Ueber die chemische Zusammensetzung der Eiterzellen" [On the chemical composition of pus cells]. Medicinisch-chemische Untersuchungen (in German). 4: 441–60.
[p. 456] Ich habe mich daher später mit meinen Versuchen an die ganzen Kerne gehalten, die Trennung der Körper, die ich einstweilen ohne weiteres Präjudiz als lösliches und unlösliches Nuclein bezeichnen will, einem günstigeren Material überlassend. (Therefore, in my experiments I subsequently limited myself to the whole nucleus, leaving to a more favorable material the separation of the substances, that for the present, without further prejudice, I will designate as soluble and insoluble nuclear material ("Nuclein"))
- ^ Dahm R (January 2008). "Discovering DNA: Friedrich Miescher and the early years of nucleic acid research". Human Genetics. 122 (6): 565–81. doi:10.1007/s00439-007-0433-0. PMID 17901982. S2CID 915930.
- ^ See:
- Kossel A (1879). "Ueber Nucleïn der Hefe" [On nuclein in yeast]. Zeitschrift für physiologische Chemie (in German). 3: 284–91.
- Kossel A (1880). "Ueber Nucleïn der Hefe II" [On nuclein in yeast, Part 2]. Zeitschrift für physiologische Chemie (in German). 4: 290–95.
- Kossel A (1881). "Ueber die Verbreitung des Hypoxanthins im Thier- und Pflanzenreich" [On the distribution of hypoxanthins in the animal and plant kingdoms]. Zeitschrift für physiologische Chemie (in German). 5: 267–71.
- Kossel A (1881). Trübne KJ (ed.). Untersuchungen über die Nucleine und ihre Spaltungsprodukte [Investigations into nuclein and its cleavage products] (in German). Strassburg, Germany. p. 19.
- Kossel A (1882). "Ueber Xanthin und Hypoxanthin" [On xanthin and hypoxanthin]. Zeitschrift für physiologische Chemie. 6: 422–31.
- Albrect Kossel (1883) "Zur Chemie des Zellkerns" Archived 17 November 2017 at the Wayback Machine (On the chemistry of the cell nucleus), Zeitschrift für physiologische Chemie, 7 : 7–22.
- Kossel A (1886). "Weitere Beiträge zur Chemie des Zellkerns" [Further contributions to the chemistry of the cell nucleus]. Zeitschrift für Physiologische Chemie (in German). 10: 248–64.
On p. 264, Kossel remarked presciently: Der Erforschung der quantitativen Verhältnisse der vier stickstoffreichen Basen, der Abhängigkeit ihrer Menge von den physiologischen Zuständen der Zelle, verspricht wichtige Aufschlüsse über die elementaren physiologisch-chemischen Vorgänge. (The study of the quantitative relations of the four nitrogenous bases—[and] of the dependence of their quantity on the physiological states of the cell—promises important insights into the fundamental physiological-chemical processes.)
- ^ Jones ME (September 1953). "Albrecht Kossel, a biographical sketch". The Yale Journal of Biology and Medicine. 26 (1): 80–97. PMC 2599350. PMID 13103145.
- ^ Levene PA, Jacobs WA (1909). "Über Inosinsäure". Berichte der Deutschen Chemischen Gesellschaft (in German). 42: 1198–203. doi:10.1002/cber.190904201196.
- ^ Levene PA, Jacobs WA (1909). "Über die Hefe-Nucleinsäure". Berichte der Deutschen Chemischen Gesellschaft (in German). 42 (2): 2474–78. doi:10.1002/cber.190904202148.
- ^ Levene P (1919). "The structure of yeast nucleic acid". J Biol Chem. 40 (2): 415–24. doi:10.1016/S0021-9258(18)87254-4.
- ^ Cohen JS, Portugal FH (1974). "The search for the chemical structure of DNA" (PDF). Connecticut Medicine. 38 (10): 551–52, 554–57. PMID 4609088.
- ^ Koltsov proposed that a cell's genetic information was encoded in a long chain of amino acids. See:
- Кольцов, Н. К. (12 December 1927). Физико-химические основы морфологии [The physical-chemical basis of morphology] (Speech). 3rd All-Union Meeting of Zoologist, Anatomists, and Histologists (in Russian). Leningrad, U.S.S.R.
- Reprinted in: Кольцов, Н. К. (1928). "Физико-химические основы морфологии" [The physical-chemical basis of morphology]. Успехи экспериментальной биологии (Advances in Experimental Biology) series B (in Russian). 7 (1): ?.
- Reprinted in German as: Koltzoff NK (1928). "Physikalisch-chemische Grundlagen der Morphologie" [The physical-chemical basis of morphology]. Biologisches Zentralblatt (in German). 48 (6): 345–69.
- In 1934, Koltsov contended that the proteins that contain a cell's genetic information replicate. See: Koltzoff N (October 1934). "The structure of the chromosomes in the salivary glands of Drosophila". Science. 80 (2075): 312–13. Bibcode:1934Sci....80..312K. doi:10.1126/science.80.2075.312. PMID 17769043.
From page 313: "I think that the size of the chromosomes in the salivary glands [of Drosophila] is determined through the multiplication of genonemes. By this term I designate the axial thread of the chromosome, in which the geneticists locate the linear combination of genes; … In the normal chromosome there is usually only one genoneme; before cell-division this genoneme has become divided into two strands."
- ^ Soyfer VN (September 2001). "The consequences of political dictatorship for Russian science". Nature Reviews Genetics. 2 (9): 723–29. doi:10.1038/35088598. PMID 11533721. S2CID 46277758.
- ^ Griffith F (January 1928). "The Significance of Pneumococcal Types". The Journal of Hygiene. 27 (2): 113–59. doi:10.1017/S0022172400031879. PMC 2167760. PMID 20474956.
- ^ Lorenz MG, Wackernagel W (September 1994). "Bacterial gene transfer by natural genetic transformation in the environment". Microbiological Reviews. 58 (3): 563–602. doi:10.1128/MMBR.58.3.563-602.1994. PMC 372978. PMID 7968924.
- ^ Brachet J (1933). "Recherches sur la synthese de l'acide thymonucleique pendant le developpement de l'oeuf d'Oursin". Archives de Biologie (in Italian). 44: 519–76.
- ^ Burian R (1994). "Jean Brachet's Cytochemical Embryology: Connections with the Renovation of Biology in France?" (PDF). In Debru C, Gayon J, Picard JF (eds.). Les sciences biologiques et médicales en France 1920–1950. Cahiers pour I'histoire de la recherche. 2. Paris: CNRS Editions. pp. 207–20.
- ^ See:
- Astbury WT, Bell FO (1938). "Some recent developments in the X-ray study of proteins and related structures" (PDF). Cold Spring Harbor Symposia on Quantitative Biology. 6: 109–21. doi:10.1101/sqb.1938.006.01.013. Archived from the original (PDF) on 14 July 2014.
- Astbury WT (1947). "X-ray studies of nucleic acids". Symposia of the Society for Experimental Biology (1): 66–76. PMID 20257017. Archived from the original on 5 July 2014.
- ^ Avery OT, Macleod CM, McCarty M (February 1944). "Studies on the Chemical Nature of the Substance Inducing Transformation of Pneumococcal Types: Induction of Transformation by a Desoxyribonucleic Acid Fraction Isolated from Pneumococcus Type III". The Journal of Experimental Medicine. 79 (2): 137–58. doi:10.1084/jem.79.2.137. PMC 2135445. PMID 19871359.
- ^ Chargaff, Erwin (June 1950). "Chemical specificity of nucleic acids and mechanism of their enzymatic degradation". Experientia. 6 (6): 201–209. doi:10.1007/BF02173653. PMID 15421335. S2CID 2522535.
- ^ Kresge, Nicole; Simoni, Robert D.; Hill, Robert L. (June 2005). "Chargaff's Rules: the Work of Erwin Chargaff". Journal of Biological Chemistry. 280 (24): 172–174. doi:10.1016/S0021-9258(20)61522-8.
- ^ Hershey AD, Chase M (May 1952). "Independent functions of viral protein and nucleic acid in growth of bacteriophage". The Journal of General Physiology. 36 (1): 39–56. doi:10.1085/jgp.36.1.39. PMC 2147348. PMID 12981234.
- ^ The B-DNA X-ray pattern on the right of this linked image Archived 25 May 2012 at archive.today
- ^ Schwartz J (2008). In pursuit of the gene : from Darwin to DNA. Cambridge, Mass.: Harvard University Press. ISBN 9780674026704.
- ^ Pauling L, Corey RB (February 1953). "A Proposed Structure For The Nucleic Acids". Proceedings of the National Academy of Sciences of the United States of America. 39 (2): 84–97. Bibcode:1953PNAS...39...84P. doi:10.1073/pnas.39.2.84. PMC 1063734. PMID 16578429.
- ^ Regis E (2009). What Is Life?: investigating the nature of life in the age of synthetic biology. Oxford: Oxford University Press. p. 52. ISBN 978-0-19-538341-6.
- ^ "Double Helix of DNA: 50 Years". Nature Archives. Archived from the original on 5 April 2015.
- ^ "Original X-ray diffraction image". Oregon State Library. Archived from the original on 30 January 2009. Retrieved 6 February 2011.
- ^ "The Nobel Prize in Physiology or Medicine 1962". Nobelprize.org.
- ^ Maddox B (January 2003). "The double helix and the 'wronged heroine'" (PDF). Nature. 421 (6921): 407–08. Bibcode:2003Natur.421..407M. doi:10.1038/nature01399. PMID 12540909. S2CID 4428347. Archived (PDF) from the original on 17 October 2016.
- ^ Crick F (1955). A Note for the RNA Tie Club (PDF) (Speech). Cambridge, England. Archived from the original (PDF) on 1 October 2008.
- ^ Meselson M, Stahl FW (July 1958). "The Replication of DNA in Escherichia Coli". Proceedings of the National Academy of Sciences of the United States of America. 44 (7): 671–82. Bibcode:1958PNAS...44..671M. doi:10.1073/pnas.44.7.671. PMC 528642. PMID 16590258.
- ^ "The Nobel Prize in Physiology or Medicine 1968". Nobelprize.org.
- ^ Pray L (2008). "Discovery of DNA structure and function: Watson and Crick". Nature Education. 1 (1): 100.
Further reading
- Berry A, Watson J (2003). DNA: the secret of life. New York: Alfred A. Knopf. ISBN 0-375-41546-7.
- Calladine CR, Drew HR, Luisi BF, Travers AA (2003). Understanding DNA: the molecule & how it works. Amsterdam: Elsevier Academic Press. ISBN 0-12-155089-3.
- Carina D, Clayton J (2003). 50 years of DNA. Basingstoke: Palgrave Macmillan. ISBN 1-4039-1479-6.
- Judson HF (1979). The Eighth Day of Creation: Makers of the Revolution in Biology (2nd ed.). Cold Spring Harbor Laboratory Press. ISBN 0-671-22540-5.
- Olby RC (1994). The path to the double helix: the discovery of DNA. New York: Dover Publications. ISBN 0-486-68117-3. First published in October 1974 by MacMillan, with foreword by Francis Crick; the definitive DNA textbook, revised in 1994 with a nine-page postscript.
- Olby R (January 2003). "Quiet debut for the double helix". Nature. 421 (6921): 402–05. Bibcode:2003Natur.421..402O. doi:10.1038/nature01397. PMID 12540907.
- Olby RC (2009). Francis Crick: A Biography. Plainview, N.Y: Cold Spring Harbor Laboratory Press. ISBN 978-0-87969-798-3.
- Micklas D (2003). DNA Science: A First Course. Cold Spring Harbor Press. ISBN 978-0-87969-636-8.
- Ridley M (2006). Francis Crick: discoverer of the genetic code. Ashland, OH: Eminent Lives, Atlas Books. ISBN 0-06-082333-X.
- Rosenfeld I (2010). DNA: A Graphic Guide to the Molecule that Shook the World. Columbia University Press. ISBN 978-0-231-14271-7.
- Schultz M, Cannon Z (2009). The Stuff of Life: A Graphic Guide to Genetics and DNA. Hill and Wang. ISBN 978-0-8090-8947-5.
- Stent GS, Watson J (1980). The Double Helix: A Personal Account of the Discovery of the Structure of DNA. New York: Norton. ISBN 0-393-95075-1.
- Watson J (2004). DNA: The Secret of Life. Random House. ISBN 978-0-09-945184-6.
- Wilkins M (2003). The third man of the double helix the autobiography of Maurice Wilkins. Cambridge, England: University Press. ISBN 0-19-860665-6.
External links
| Library resources about DNA |
|
| Wikiquote has quotations related to: DNA |
| Wikiversity has learning resources about DNA |
| Wikimedia Commons has media related to DNA. |
- DNA at Curlie
- DNA binding site prediction on protein
- DNA the Double Helix Game From the official Nobel Prize web site
- DNA under electron microscope
- Dolan DNA Learning Center
- Double Helix: 50 years of DNA, Nature
- Proteopedia DNA
- Proteopedia Forms_of_DNA
- ENCODE threads explorer ENCODE home page. Nature
- Double Helix 1953–2003 National Centre for Biotechnology Education
- Genetic Education Modules for Teachers – DNA from the Beginning Study Guide
- PDB Molecule of the Month DNA
- "Clue to chemistry of heredity found". The New York Times, June 1953. First American newspaper coverage of the discovery of the DNA structure
- DNA from the Beginning Another DNA Learning Center site on DNA, genes, and heredity from Mendel to the human genome project.
- The Register of Francis Crick Personal Papers 1938 – 2007 at Mandeville Special Collections Library, University of California, San Diego
- Seven-page, handwritten letter that Crick sent to his 12-year-old son Michael in 1953 describing the structure of DNA. See Crick's medal goes under the hammer, Nature, 5 April 2013.
- DNA
- Helices
- Biotechnology
- Nucleic acids